Homología de secuencia

Homología de secuencia es la homología biológica entre secuencias de ADN, ARN o proteínas, definida en términos de ascendencia compartida en la historia evolutiva de la vida. Dos segmentos de ADN pueden tener ascendencia compartida debido a tres fenómenos: ya sea un evento de especiación (ortólogos), o un evento de duplicación (parálogos), o bien un evento de transferencia genética horizontal (o lateral) (xenólogos).
La homología entre el ADN, el ARN o las proteínas normalmente se infiere a partir de la similitud de la secuencia de nucleótidos o aminoácidos. Una similitud significativa es una fuerte evidencia de que dos secuencias están relacionadas por cambios evolutivos a partir de una secuencia ancestral común. Se utilizan alineaciones de múltiples secuencias para indicar qué regiones de cada secuencia son homólogas.
Identidad, similitud y conservación

El término "porcentaje de homología" se utiliza a menudo para significar "similitud de secuencia", es decir, el porcentaje de residuos idénticos (porcentaje de identidad), o el porcentaje de residuos conservados con propiedades fisicoquímicas similares (porcentaje de similitud). i>), p.e. leucina e isoleucina, generalmente se usa para "cuantificar la homología". Según la definición de homología especificada anteriormente, esta terminología es incorrecta ya que la similitud de secuencia es la observación y la homología es la conclusión. Las secuencias son homólogas o no. Esto implica que el término "porcentaje de homología" es un nombre inapropiado.
Al igual que con las estructuras morfológicas y anatómicas, la similitud de secuencia puede ocurrir debido a una evolución convergente o, como ocurre con las secuencias más cortas, por casualidad, lo que significa que no son homólogas. Las regiones de secuencias homólogas también se denominan conservadas. Esto no debe confundirse con la conservación en secuencias de aminoácidos, donde el aminoácido en una posición específica se ha sustituido por uno diferente que tiene propiedades fisicoquímicas funcionalmente equivalentes.
Puede ocurrir una homología parcial cuando un segmento de las secuencias comparadas tiene un origen compartido, mientras que el resto no. Esta homología parcial puede resultar de un evento de fusión genética.
Ortología

Las secuencias homologosas son ortologosas si se infiere a descender de la misma secuencia ancestral separada por un evento de especulación: cuando una especie se sumerge en dos especies separadas, se dice que las copias de un solo gen en las dos especies resultantes son ortologosas. Los ortologs, o genes ortologosos, son genes en diferentes especies que se originaron por ascendencia vertical de un único gen del último ancestro común. El término "ortolog" fue acuñado en 1970 por el evolucionista molecular Walter Fitch.
Por ejemplo, la proteína vegetal reguladora de la gripe está presente tanto en Arabidopsis (planta superior multicelular) como en Chlamydomonas (alga verde unicelular). La versión de Chlamydomonas es más compleja: cruza la membrana dos veces en lugar de una, contiene dominios adicionales y se somete a un empalme alternativo. Sin embargo, puede sustituir completamente a la proteína Arabidopsis, mucho más simple, si se transfiere del genoma de las algas al genoma de las plantas mediante ingeniería genética. La similitud de secuencia significativa y los dominios funcionales compartidos indican que estos dos genes son genes ortólogos, heredados del ancestro compartido.
La ortología está estrictamente definida en términos de ascendencia. Dado que es difícil determinar la ascendencia exacta de genes en diferentes organismos debido a la duplicación de genes y a eventos de reordenamiento del genoma, la evidencia más sólida de que dos genes similares son ortólogos generalmente se encuentra realizando un análisis filogenético del linaje de genes. Los ortólogos suelen, pero no siempre, tener la misma función.
Las secuencias ortólogas proporcionan información útil en la clasificación taxonómica y estudios filogenéticos de organismos. El patrón de divergencia genética se puede utilizar para rastrear la relación de los organismos. Es probable que dos organismos que están muy relacionados muestren secuencias de ADN muy similares entre dos ortólogos. Por el contrario, un organismo que está más alejado evolutivamente de otro organismo probablemente muestre una mayor divergencia en la secuencia de los ortólogos que se estudian.
Bases de datos de genes ortólogos
Dada su tremenda importancia para la biología y la bioinformática, los genes ortólogos se han organizado en varias bases de datos especializadas que proporcionan herramientas para identificar y analizar secuencias de genes ortólogos. Estos recursos emplean enfoques que generalmente se pueden clasificar en aquellos que utilizan análisis heurístico de todas las comparaciones de secuencias por pares y aquellos que utilizan métodos filogenéticos. Los métodos de comparación de secuencias fueron pioneros en la base de datos COG en 1997. Estos métodos se han ampliado y automatizado en doce bases de datos diferentes, siendo la más avanzada AYbRAH Analyzing Yeasts by Reconstructing Ancestry of Homologs, así como las siguientes bases de datos en este momento.
- eggNOG
- GreenPhylDB para plantas
- InParanoid se centra en relaciones ortolog pares
- OHNOLOGS es un repositorio de los genes retenidos de duplicaciones enteras del genoma en los genomas vertebrados incluyendo humanos y ratón.
- OMA
- OrthoDB aprecia que el concepto de ortología es relativo a diferentes puntos de especulación proporcionando una jerarquía de ortologs a lo largo del árbol de especies.
- OrthoInspector es un repositorio de genes ortologosos para 4753 organismos que cubren los tres dominios de la vida
- OrthologID
- OrthoMa M para mamíferos
- OrthoMCL
- Roundup
Los enfoques filogenéticos basados en árboles tienen como objetivo distinguir la especiación de los eventos de duplicación de genes comparando árboles de genes con árboles de especies, tal como se implementa en bases de datos y herramientas de software como:
- LOFT
- TreeFam
- OrthoFinder
Una tercera categoría de enfoques híbridos utiliza métodos tanto heurísticos como filogenéticos para construir grupos y determinar árboles, por ejemplo:
- EnsemblCompara GeneTrees
- HomoloGene
- Ortholuge
Paralogy
Los genes parálogos son genes que se relacionan mediante eventos de duplicación en el último ancestro común (LCA) de la especie que se compara. Resultan de la mutación de genes duplicados durante eventos de especiación separados. Cuando los descendientes de LCA comparten homólogos mutados de los genes duplicados originales, esos genes se consideran parálogos.
Como ejemplo, en el LCA, un gen (gen A) puede duplicarse para formar un gen similar (gen B); esos dos genes continuarán transmitiéndose a las generaciones siguientes. Durante la especiación, un ambiente favorecerá una mutación en el gen A (gen A1), produciendo una nueva especie con los genes A1 y B. Luego, en un evento de especiación separado, un ambiente favorecerá una mutación en el gen B (gen B1) dando lugar a una nueva especie con genes A y B1. Los descendientes' Los genes A1 y B1 son parálogos entre sí porque son homólogos que están relacionados mediante un evento de duplicación en el último ancestro común de las dos especies.
Las clasificaciones adicionales de parálogos incluyen aloparálogos (parálogos externos) y simparalogos (parálogos internos). Los aloparálogos son parálogos que evolucionaron a partir de duplicaciones de genes que precedieron al evento de especiación dado. En otras palabras, los aloparálogos son parálogos que evolucionaron a partir de eventos de duplicación que ocurrieron en el ACV de los organismos que se comparan. El ejemplo anterior es un ejemplo de aloparalogía. Los simparalogos son parálogos que evolucionaron a partir de la duplicación de genes parálogos en eventos de especiación posteriores. Según el ejemplo anterior, si el descendiente con los genes A1 y B sufriera otro evento de especiación en el que el gen A1 se duplicara, la nueva especie tendría los genes B, A1a y A1b. En este ejemplo, los genes A1a y A1b son simpalogos.
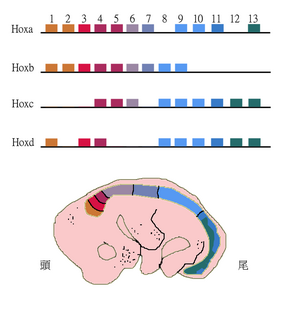
Los genes parálogos pueden dar forma a la estructura de genomas completos y, por tanto, explicar en gran medida la evolución del genoma. Los ejemplos incluyen los genes Homeobox (Hox) en animales. Estos genes no sólo experimentaron duplicaciones genéticas dentro de los cromosomas sino también duplicaciones del genoma completo. Como resultado, los genes Hox en la mayoría de los vertebrados están agrupados en múltiples cromosomas, siendo los grupos HoxA-D los mejor estudiados.
Otro ejemplo son los genes de globina que codifican la mioglobina y la hemoglobina y se consideran parálogos antiguos. De manera similar, las cuatro clases conocidas de hemoglobinas (hemoglobina A, hemoglobina A2, hemoglobina B y hemoglobina F) son parálogos entre sí. Si bien cada una de estas proteínas cumple la misma función básica de transporte de oxígeno, sus funciones ya han divergido ligeramente: la hemoglobina fetal (hemoglobina F) tiene una mayor afinidad por el oxígeno que la hemoglobina adulta. Sin embargo, la función no siempre se conserva. La angiogenina humana se separó de la ribonucleasa, por ejemplo, y aunque los dos parálogos siguen siendo similares en su estructura terciaria, sus funciones dentro de la célula son ahora bastante diferentes.
A menudo se afirma que los ortólogos son más similares funcionalmente que los parálogos de divergencia similar, pero varios artículos han cuestionado esta noción.
Reglamento
Los parálogos a menudo se regulan de manera diferente, p. al tener diferentes patrones de expresión específicos de tejido (ver genes Hox). Sin embargo, también pueden regularse de forma diferente a nivel de proteínas. Por ejemplo, Bacillus subtilis codifica dos parálogos de la glutamato deshidrogenasa: GudB se transcribe constitutivamente mientras que RocG está estrictamente regulado. En sus estados oligoméricos activos, ambas enzimas muestran tasas enzimáticas similares. Sin embargo, los intercambios de enzimas y promotores provocan graves pérdidas de aptitud física, lo que indica una coevolución promotor-enzima. La caracterización de las proteínas muestra que, en comparación con RocG, la actividad enzimática de GudB depende en gran medida del glutamato y el pH.
regiones cromosómicas parálogas
A veces, grandes regiones de los cromosomas comparten contenido genético similar a otras regiones cromosómicas dentro del mismo genoma. Están bien caracterizados en el genoma humano, donde se han utilizado como evidencia para apoyar la hipótesis 2R. Se deduce que conjuntos de genes duplicados, triplicados y cuadruplicados, con los genes relacionados en diferentes cromosomas, son restos del genoma o duplicaciones cromosómicas. Un conjunto de regiones paralógicas se denomina en conjunto paralogon. Los conjuntos de regiones paralógicas bien estudiados incluyen regiones del cromosoma humano 2, 7, 12 y 17 que contienen grupos de genes Hox, genes de colágeno, genes de queratina y otros genes duplicados, regiones de los cromosomas humanos 4, 5, 8 y 10 que contienen genes de receptores de neuropéptidos, Genes homeobox de clase NK y muchas más familias de genes, y partes de los cromosomas humanos 13, 4, 5 y X que contienen los genes ParaHox y sus vecinos. El complejo mayor de histocompatibilidad (MHC) en el cromosoma 6 humano tiene regiones paralógicas en los cromosomas 1, 9 y 19. Gran parte del genoma humano parece asignarse a regiones paralógicas.
Ohnología
Los genes ohnólogos son genes parálogos que se han originado mediante un proceso de duplicación de todo el genoma. El nombre fue dado por primera vez en honor a Susumu Ohno por Ken Wolfe. Los ohnólogos son útiles para el análisis evolutivo porque todos los ohnólogos de un genoma han divergido durante el mismo período de tiempo (desde su origen común en la duplicación de todo el genoma). También se sabe que los ohnólogos muestran una mayor asociación con cánceres, trastornos genéticos dominantes y variaciones en el número de copias patógenas.
Xenología
Los homólogos resultantes de la transferencia horizontal de genes entre dos organismos se denominan xenólogos. Los xenólogos pueden tener diferentes funciones si el nuevo entorno es muy diferente para el gen que se mueve horizontalmente. Sin embargo, en general, los xenólogos suelen tener funciones similares en ambos organismos. El término fue acuñado por Walter Fitch.
Homeología
Los cromosomas o partes de cromosomas homólogos (también escritos como homeólogos) son aquellos que se reúnen después de una hibridación y alopoliploidización entre especies para formar un genoma híbrido, y cuya relación era completamente homóloga en una especie ancestral. En los alopoliploides, los cromosomas homólogos dentro de cada subgenoma parental deben emparejarse fielmente durante la meiosis, lo que lleva a la herencia disómica; sin embargo, en algunos alopoliploides, los cromosomas homólogos de los genomas parentales pueden ser casi tan similares entre sí como los cromosomas homólogos, lo que lleva a herencia tetrasómica (cuatro cromosomas apareados en la meiosis), recombinación intergenómica y fertilidad reducida.
Gametología
Gametology denota la relación entre genes homologosos en cromosomas sexuales no recombinantes, opuestos. El término fue acuñado por García-Moreno y Mindell. 2000. Gametologs resulta de la originación de determinación del sexo genético y barreras a la recombinación entre cromosomas sexuales. Ejemplos de gametologs incluyen CHDW y CHDZ en aves.
Contenido relacionado
Ley de Fick
Híbrido (biología)
Evolución divergente


