Visualización de fagos
presentación en fagos es una técnica de laboratorio para el estudio de las interacciones proteína-proteína, proteína-péptido y proteína-ADN que utiliza bacteriófagos (virus que infectan bacterias) para conectar las proteínas con la información genética que los codifica. En esta técnica, un gen que codifica una proteína de interés se inserta en un gen de la proteína de la cubierta del fago, lo que hace que el fago "muestre" la proteína en su exterior mientras que contiene el gen de la proteína en su interior, lo que resulta en una conexión entre genotipo y fenotipo. Las proteínas que presentan los fagos pueden luego compararse con otras proteínas, péptidos o secuencias de ADN, para detectar la interacción entre la proteína presentada y las de otras moléculas. De esta manera, se pueden seleccionar y amplificar grandes bibliotecas de proteínas en un proceso llamado selección in vitro, que es análogo a la selección natural.
Los bacteriófagos más comunes utilizados en la presentación de fagos son los fagos filamentosos M13 y fd, aunque también se han utilizado los fagos T4, T7 y λ.
Historia
La presentación en fagos fue descrita por primera vez por George P. Smith en 1985, cuando demostró la presentación de péptidos en fagos filamentosos (virus largos y delgados que infectan bacterias) fusionando la proteína de la cápside del virus con un péptido de una colección de secuencias peptídicas. Esto mostró los diferentes péptidos en las superficies exteriores de la colección de clones virales, donde el paso de selección del proceso aisló los péptidos con la mayor afinidad de unión. En 1988, Stephen Parmley y George Smith describieron la biopanning para la selección por afinidad y demostraron que las rondas recursivas de selección podrían enriquecer clones presentes en 1 entre mil millones o menos. En 1990, Jamie Scott y George Smith describieron la creación de grandes bibliotecas de péptidos aleatorios exhibidos en fagos filamentosos. La tecnología de visualización de fagos fue desarrollada y mejorada por grupos del Laboratorio de Biología Molecular con Greg Winter y John McCafferty, el Instituto de Investigación Scripps con Richard Lerner y Carlos Barbas y el Centro Alemán de Investigación del Cáncer con Frank Breitling y Stefan Dübel para la visualización de proteínas como como anticuerpos para la ingeniería de proteínas terapéuticas. Smith y Winter recibieron la mitad del Premio Nobel de Química 2018 por su contribución al desarrollo de la visualización de fagos. Una patente de George Pieczenik que reclama prioridad desde 1985 también describe la generación de bibliotecas de péptidos.
Principio
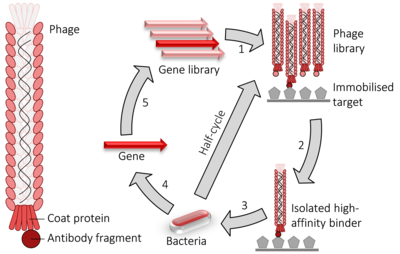
Al igual que el sistema de dos híbridos, la presentación en fagos se utiliza para la detección de alto rendimiento de interacciones entre proteínas. En el caso de la presentación en fagos filamentosos M13, el ADN que codifica la proteína o el péptido de interés se liga al gen pIII o pVIII, que codifica la proteína de cubierta menor o mayor, respectivamente. A veces se utilizan múltiples sitios de clonación para garantizar que los fragmentos se inserten en los tres marcos de lectura posibles para que el fragmento de ADNc se traduzca en el marco adecuado. Luego, el gen del fago y el híbrido de ADN insertado se insertan (un proceso conocido como "transducción") en E. coli células bacterianas como TG1, SS320, ER2738 o XL1-Blue E. coli. Si un "fagémido" Si se utiliza un vector (un vector de construcción de visualización simplificado), las partículas de fago no se liberarán del E. coli hasta que se infectan con el fago auxiliar, lo que permite el empaquetado del ADN del fago y el ensamblaje de los viriones maduros con el fragmento proteico relevante como parte de su capa externa, ya sea en el fago menor (pIII) o en el mayor (pVIII). proteína de cubierta. Al inmovilizar una diana relevante de ADN o proteína en la superficie de un pocillo de placa de microtitulación, un fago que muestra una proteína que se une a una de esas dianas en su superficie permanecerá mientras que otras se eliminan mediante lavado. Los que quedan pueden eluirse, usarse para producir más fagos (mediante infección bacteriana con fagos auxiliares) y para producir una mezcla de fagos que se enriquece con fagos relevantes (es decir, de unión). El ciclo repetido de estos pasos se conoce como "lavado", en referencia al enriquecimiento de una muestra de oro mediante la eliminación de materiales indeseables. El fago eluido en el paso final se puede utilizar para infectar un huésped bacteriano adecuado, del cual se pueden recolectar los fagémidos y se puede escindir y secuenciar la secuencia de ADN relevante para identificar las proteínas o fragmentos de proteínas relevantes que interactúan.
El uso de un fago auxiliar se puede eliminar mediante el uso de una 'línea celular de empaquetamiento bacteriano' tecnología.
La elución se puede realizar combinando un tampón de elución de pH bajo con sonificación, que, además de aflojar la interacción péptido-objetivo, también sirve para separar la molécula objetivo de la superficie de inmovilización. Este método basado en ultrasonido permite la selección en un solo paso de un péptido de alta afinidad.
Aplicaciones
Las aplicaciones de la tecnología de presentación en fagos incluyen la determinación de las parejas de interacción de una proteína (que se utilizaría como "cebo" del fago inmovilizado con una biblioteca de ADN que consta de todas las secuencias codificantes de una célula, tejido u organismo). para que se pueda determinar la función o el mecanismo de función de esa proteína. La presentación en fagos también es un método ampliamente utilizado para la evolución de proteínas in vitro (también llamada ingeniería de proteínas). Como tal, la presentación en fagos es una herramienta útil en el descubrimiento de fármacos. Se utiliza para encontrar nuevos ligandos (inhibidores de enzimas, agonistas y antagonistas de receptores) para atacar proteínas. La técnica también se utiliza para determinar antígenos tumorales (para uso en diagnóstico y orientación terapéutica) y en la búsqueda de interacciones proteína-ADN utilizando bibliotecas de ADN especialmente construidas con segmentos aleatorizados. Recientemente, la presentación en fagos también se ha utilizado en el contexto de tratamientos contra el cáncer, como el método de transferencia celular adoptiva. En estos casos, la presentación en fagos se utiliza para crear y seleccionar anticuerpos sintéticos que se dirigen a las proteínas de la superficie del tumor. Estos se convierten en receptores sintéticos para las células T recolectadas del paciente que se utilizan para combatir la enfermedad.
Los métodos competitivos para la evolución de proteínas in vitro incluyen la visualización de levaduras, la visualización de bacterias, la visualización de ribosomas y la visualización de ARNm.
Maduración de anticuerpos in vitro
La invención de la presentación en fagos de anticuerpos revolucionó el descubrimiento de fármacos con anticuerpos. El trabajo inicial fue realizado por laboratorios del Laboratorio de Biología Molecular del MRC (Greg Winter y John McCafferty), el Instituto de Investigación Scripps (Richard Lerner y Carlos F. Barbas) y el Centro Alemán de Investigación del Cáncer (Frank Breitling y Stefan Dübel). En 1991, el grupo Scripps informó sobre la primera visualización y selección de anticuerpos humanos en fagos. Este estudio inicial describió el aislamiento rápido del anticuerpo humano Fab que se une a la toxina tetánica y luego el método se amplió para clonar rápidamente anticuerpos humanos anti-VIH-1 para el diseño y la terapia de vacunas.
La presentación en fagos de bibliotecas de anticuerpos se ha convertido en un método poderoso tanto para estudiar la respuesta inmune como para seleccionar y desarrollar rápidamente anticuerpos humanos para terapia. Carlos F. Barbas en el Instituto de Investigación Scripps utilizó posteriormente la presentación en fagos de anticuerpos para crear bibliotecas de anticuerpos humanos sintéticos, un principio patentado por primera vez en 1990 por Breitling y sus colaboradores (Patente CA 2035384), lo que permite crear anticuerpos humanos in vitro a partir de anticuerpos sintéticos. elementos de diversidad.
Las bibliotecas de anticuerpos que muestran millones de anticuerpos diferentes en fagos se utilizan a menudo en la industria farmacéutica para aislar anticuerpos terapéuticos altamente específicos, para su desarrollo en fármacos de anticuerpos principalmente como terapias anticancerígenas o antiinflamatorias. Uno de los más exitosos fue el adalimumab, descubierto por Cambridge Antibody Technology como D2E7 y desarrollado y comercializado por Abbott Laboratories. Adalimumab, un anticuerpo contra el TNF alfa, fue el primer anticuerpo totalmente humano del mundo en alcanzar ventas anuales superiores a los mil millones de dólares.
Protocolo general
A continuación se muestra la secuencia de eventos que se siguen en la detección de presentación de fagos para identificar polipéptidos que se unen con alta afinidad a la proteína objetivo o secuencia de ADN deseada:
- Las proteínas de blanco o las secuencias de ADN se inmovilizan en los pozos de una placa microtiter.
- Muchas secuencias genéticas se expresan en una biblioteca de bacteriófagos en forma de fusiones con la proteína de la capa de bacteriófago, de modo que se muestran en la superficie de la partícula viral. La proteína mostrada corresponde a la secuencia genética dentro del phage.
- Esta biblioteca de phage-display se añade al plato y después de permitir el tiempo de phage para atar, el plato se lava.
- Las proteínas que reproducen el Phage que interactúan con las moléculas dianas permanecen unidas al plato, mientras que todas las demás se lavan.
- Se puede eludir y usar el phage adjunto para crear más phage por infección de anfitriones bacterianos adecuados. El nuevo phage constituye una mezcla enriquecida, que contiene un phage considerablemente menos irrelevante (es decir, no vinculante) de lo que estaba presente en la mezcla inicial.
- Los pasos 3 a 5 se repiten opcionalmente una o más veces, enriqueciendo aún más la biblioteca de phage en proteínas vinculantes.
- Después de una amplificación basada en bacterias, se secuencia el ADN dentro de la faja de interacción para identificar las proteínas o fragmentos de proteínas que interactúan.
Selección de la proteína de cubierta
Fagos filamentosos
PIII
pIII es la proteína que determina la infectividad del virión. pIII se compone de tres dominios (N1, N2 y CT) conectados por conectores ricos en glicina. El dominio N2 se une al pilus F durante la infección del virión liberando el dominio N1 que luego interactúa con una proteína TolA en la superficie de la bacteria. Las inserciones dentro de esta proteína generalmente se agregan en la posición 249 (dentro de una región conectora entre CT y N2), la posición 198 (dentro del dominio N2) y en el extremo N (insertado entre la secuencia de secreción N-terminal y el extremo N-terminal de pIII). Sin embargo, cuando se utiliza el sitio BamHI ubicado en la posición 198, se debe tener cuidado con el residuo de cisteína no apareado (C201) que podría causar problemas durante la presentación en fagos si se usa una versión no truncada de pIII.
Una ventaja de usar pIII en lugar de pVIII es que pIII permite la presentación monovalente cuando se usa un fagémido (plásmido derivado de fagos Ff) combinado con un fago auxiliar. Además, pIII permite la inserción de secuencias de proteínas más grandes (>100 aminoácidos) y es más tolerante a la misma que pVIII. Sin embargo, el uso de pIII como compañero de fusión puede provocar una disminución en la infectividad del fago, lo que genera problemas como el sesgo de selección causado por la diferencia en la tasa de crecimiento del fago o, peor aún, la incapacidad del fago para infectar a su huésped. La pérdida de infectividad del fago se puede evitar utilizando un plásmido fagémido y un fago auxiliar de modo que el fago resultante contenga tanto pIII de tipo salvaje como de fusión.
El ADNc también se ha analizado utilizando pIII mediante un sistema de dos cremalleras de leucina complementarias, Direct Interaction Rescue o añadiendo un conector de 8 a 10 aminoácidos entre el ADNc y pIII en el extremo C-terminal.
PVIII
pVIII es la proteína de cubierta principal de los fagos Ff. Los péptidos suelen estar fusionados al extremo N de pVIII. Normalmente, los péptidos que pueden fusionarse con pVIII tienen entre 6 y 8 aminoácidos de longitud. La restricción de tamaño parece tener menos que ver con el impedimento estructural causado por la sección agregada y más con la exclusión de tamaño causada por pIV durante la exportación de proteína de cubierta. Dado que hay alrededor de 2700 copias de la proteína en un fago típico, es más probable que la proteína de interés se exprese de forma polivalente incluso si se utiliza un fagémido. Esto hace que el uso de esta proteína sea desfavorable para el descubrimiento de compañeros de unión de alta afinidad.
Para superar el problema del tamaño de pVIII, se han diseñado proteínas de cubierta artificiales. Un ejemplo es la proteína de cubierta artificial invertida (ACP) de Weiss y Sidhu, que permite la visualización de proteínas grandes en el extremo C-terminal. Los ACP podrían presentar una proteína de 20 kDa, sin embargo, sólo en niveles bajos (en la mayoría de los casos, sólo de forma monovalente).
PVI
pVI se ha utilizado ampliamente para la visualización de bibliotecas de ADNc. La visualización de bibliotecas de ADNc mediante presentación en fagos es una alternativa atractiva al método del híbrido de levadura 2 para el descubrimiento de proteínas y péptidos que interactúan debido a su alta capacidad de rendimiento. pVI se ha utilizado preferentemente en lugar de pVIII y pIII para la expresión de bibliotecas de ADNc porque se puede agregar la proteína de interés al extremo C de pVI sin afectar en gran medida el papel de pVI en el ensamblaje de fagos. Esto significa que el codón de parada en el ADNc ya no es un problema. Sin embargo, la presentación en fagos del ADNc siempre está limitada por la incapacidad de la mayoría de los procariotas para producir modificaciones postraduccionales presentes en las células eucariotas o por el mal plegamiento de proteínas multidominio.
Si bien pVI ha sido útil para el análisis de bibliotecas de ADNc, pIII y pVIII siguen siendo las proteínas de cubierta más utilizadas para la presentación en fagos.
PVII y pIX
En un experimento realizado en 1995, se intentó mostrar la glutatión S-transferasa tanto en pVII como en pIX y fracasó. Sin embargo, la presentación en fagos de esta proteína se completó con éxito después de la adición de una secuencia señal periplásmica (pelB u ompA) en el extremo N. En un estudio reciente, se ha demostrado que AviTag, FLAG e His podrían visualizarse en pVII sin necesidad de una secuencia de señal. Luego, la expresión de Fv de cadena simple (scFv) y de receptores de células T de cadena simple (scTCR) se expresó con y sin la secuencia señal.
PelB (una secuencia señal de aminoácidos que dirige la proteína al periplasma donde una peptidasa señal luego escinde PelB) mejoró el nivel de presentación en fagos en comparación con las fusiones pVII y pIX sin la secuencia señal. Sin embargo, esto condujo a la incorporación de más genomas de fagos auxiliares en lugar de genomas de fagémidos. En todos los casos, los niveles de presentación en fagos fueron más bajos que cuando se utilizó la fusión pIII. Sin embargo, una visualización más baja podría ser más favorable para la selección de aglutinantes debido a que la visualización más baja se acerca más a la visualización monovalente verdadera. En cinco de seis ocasiones, las fusiones de pVII y pIX sin pelB fueron más eficientes que las fusiones de pIII en los ensayos de selección de afinidad. El documento incluso continúa afirmando que las plataformas de visualización pVII y pIX pueden superar a pIII a largo plazo.
El uso de pVII y pIX en lugar de pIII también podría ser una ventaja porque se puede realizar el rescate del virión sin romper el enlace virión-antígeno si el pIII utilizado es de tipo salvaje. En cambio, se podría escindir una sección entre la perla y el antígeno para eluir. Dado que el pIII está intacto, no importa si el antígeno permanece unido al fago.
Fagos T7
El problema del uso de fagos Ff para la presentación en fagos es que requieren que la proteína de interés se transloque a través de la membrana interna bacteriana antes de ensamblarse en el fago. Algunas proteínas no pueden someterse a este proceso y, por lo tanto, no pueden exhibirse en la superficie de los fagos Ff. En estos casos, se utiliza la presentación en fagos T7. En la presentación en fagos T7, la proteína que se va a presentar está unida al extremo C terminal de la proteína de la cápsida del gen 10 de T7.
La desventaja de usar T7 es que el tamaño de la proteína que se puede expresar en la superficie se limita a péptidos más cortos porque los grandes cambios en el genoma de T7 no se pueden acomodar como ocurre en M13, donde el fago simplemente alarga su cubierta. para encajar el genoma más grande dentro de él. Sin embargo, puede ser útil para la producción de una gran biblioteca de proteínas para la selección de scFV donde el scFV se expresa en un fago M13 y los antígenos se expresan en la superficie del fago T7.
Recursos y herramientas bioinformáticas
Las bases de datos y las herramientas computacionales para mimotopos han sido una parte importante del estudio de visualización de fagos. Se han utilizado ampliamente bases de datos, programas y servidores web para excluir péptidos no relacionados con el objetivo, caracterizar interacciones pequeñas moléculas-proteínas y mapear interacciones proteína-proteína. Los usuarios pueden utilizar la estructura tridimensional de una proteína y los péptidos seleccionados del experimento de presentación en fagos para mapear epítopos conformacionales. Algunos de los métodos computacionales rápidos y eficientes están disponibles en línea.