Sentido (biología molecular)
En biología molecular y genética, el sentido de una molécula de ácido nucleico, en particular de una cadena de ADN o ARN, se refiere a la naturaleza de las funciones de la cadena y su complemento en la especificación de una secuencia de aminoácidos. Según el contexto, el sentido puede tener significados ligeramente diferentes. Por ejemplo, la cadena de ADN de sentido negativo es equivalente a la cadena molde, mientras que la cadena de sentido positivo es la cadena no molde cuya secuencia de nucleótidos es equivalente a la secuencia de la transcripción del ARNm.
ADN sentido
Debido a la naturaleza complementaria del apareamiento de bases entre polímeros de ácidos nucleicos, una molécula de ADN bicatenario estará compuesta por dos cadenas con secuencias que son complementos inversos entre sí. Para ayudar a los biólogos moleculares a identificar específicamente cada cadena individualmente, las dos cadenas se suelen diferenciar como la cadena "sentido" y la cadena "antisentido". Una cadena individual de ADN se denomina de "sentido positivo" (también "positivo (+)" o simplemente "sentido") si su secuencia de nucleótidos corresponde directamente a la secuencia de un transcrito de ARN que se traduce o es traducible a una secuencia de aminoácidos (siempre que las bases de timina en la secuencia de ADN se reemplacen con bases de uracilo en la secuencia de ARN). La otra hebra de la molécula de ADN de doble cadena se denomina de sentido negativo (también negativo (−) o antisentido), y es complementaria inversa tanto de la hebra de sentido positivo como de la transcripción de ARN. En realidad, es la hebra antisentido la que se utiliza como plantilla a partir de la cual las ARN polimerasas construyen la transcripción de ARN, pero el apareamiento de bases complementario mediante el cual se produce la polimerización de ácidos nucleicos significa que la secuencia de la transcripción de ARN será idéntica a la hebra de sentido positivo, aparte del uso de uracilo en la transcripción de ARN en lugar de timina.
A veces, las frases cadena codificante y cadena molde se encuentran en lugar de sentido y antisentido, respectivamente, y en el contexto de una molécula de ADN bicatenario el uso de estos términos es esencialmente equivalente. Sin embargo, la cadena codificante/sentido no siempre necesita contener un código que se utiliza para crear una proteína; tanto el ARN codificante como el no codificante de proteínas pueden transcribirse.
Los términos "sentido" y "antisentido" se refieren únicamente al transcrito de ARN en cuestión, y no a la cadena de ADN en su totalidad. En otras palabras, cualquiera de las cadenas de ADN puede servir como cadena sentido o antisentido. La mayoría de los organismos con genomas suficientemente grandes utilizan ambas cadenas, y cada una de ellas funciona como cadena molde para diferentes transcripciones de ARN en diferentes lugares a lo largo de la misma molécula de ADN. En algunos casos, las transcripciones de ARN se pueden transcribir en ambas direcciones (es decir, en cualquiera de las cadenas) desde una región promotora común, o se pueden transcribir desde dentro de los intrones en cualquiera de las cadenas (véase "ambisentido" a continuación).
ADN sensorial
La cadena de ADN con sentido se parece a la transcripción del ARN mensajero (ARNm) y, por lo tanto, se puede utilizar para leer la secuencia de codones esperada que se utilizará en última instancia durante la traducción (síntesis de proteínas) para construir una secuencia de aminoácidos y luego una proteína. Por ejemplo, la secuencia "ATG" dentro de una cadena de ADN con sentido corresponde a un codón "AUG" en el ARNm, que codifica el aminoácido metionina. Sin embargo, la cadena de ADN con sentido en sí no se utiliza como plantilla para el ARNm; es la cadena de ADN antisentido la que sirve como fuente para el código de la proteína, porque, al tener bases complementarias a la cadena de ADN con sentido, se utiliza como plantilla para el ARNm. Dado que la transcripción da como resultado un producto de ARN complementario a la cadena de ADN plantilla, el ARNm es complementario a la cadena de ADN antisentido.
Por lo tanto, se utiliza como plantilla un triplete de bases 3′-TAC-5′ en la cadena antisentido del ADN (complementario al 5′-ATG-3′ de la cadena con sentido del ADN), lo que da como resultado un triplete de bases 5′-AUG-3′ en el ARNm. La cadena con sentido del ADN tendrá el triplete ATG, que se parece al triplete AUG del ARNm, pero no se utilizará para fabricar metionina porque no se utilizará directamente para fabricar ARNm. La cadena con sentido del ADN se denomina cadena "con sentido" no porque se vaya a utilizar para fabricar proteínas (no será así), sino porque tiene una secuencia que corresponde directamente a la secuencia de codones del ARN. Según esta lógica, la transcripción del ARN en sí misma a veces se describe como "con sentido".
Ejemplo con ADN de doble tirada
- Vajilla de ADN 1: hebra antisense (transcribido a) → Rango de ARN (sentido)
- Varón de ADN 2: hebra de sentido
Algunas regiones dentro de una molécula de ADN bicatenario codifican genes, que son generalmente instrucciones que especifican el orden en el que se ensamblan los aminoácidos para formar proteínas, así como secuencias reguladoras, sitios de empalme, intrones no codificantes y otros productos genéticos. Para que una célula utilice esta información, una hebra del ADN sirve como plantilla para la síntesis de una hebra complementaria de ARN. La hebra de ADN transcrita se denomina hebra plantilla, con secuencia antisentido, y la transcripción de ARNm producida a partir de ella se dice que es secuencia sentido (el complemento de la antisentido). La hebra de ADN no transcrita, complementaria a la hebra transcrita, también se dice que tiene secuencia sentido; tiene la misma secuencia sentido que la transcripción de ARNm (aunque las bases T en el ADN se sustituyen por bases U en el ARN).
3′CGCTATAGCGTTT 5′ | Varilla antisensayo de ADN (templa/no codificación) | Usado como plantilla para transcripción. |
5′GCGATATCGCAAA 3′ | Perla de ADN (no tentación/codificación) | Complementario al hilo de plantilla. |
5′GCGAUAUCGCAAA 3′ | mRNA transcripción de sentido | El hilo RNA que se transcribe de la cadena no codificación (template/antisense). Nota1: Excepto por el hecho de que todas las timinas son ahora uraciles (T → U), es complementario complementario complementario to the noncoding (template/antisense) DNA strand and idéntica a la cadena de ADN de codificación (notempla/sense).
|
3′CGCUAUAGCGUUU 5′ | mRNA transcripción antisense | Lámina de ARN que se transcribe de la cadena de codificación (notemplate/sense). Nota: Excepto por el hecho de que todas las timinas son ahora uraciles (T → U), es complementario complementario complementario to the coding (nontemplate/sense) DNA strand and idéntica a la cadena de ADN no codificación (template/antisense).
|
Los nombres asignados a cada hebra dependen en realidad de la dirección en la que se escribe la secuencia que contiene la información de las proteínas (la información de "sentido"), no de qué hebra se representa como "arriba" o "abajo" (lo cual es arbitrario). La única información biológica que es importante para etiquetar las hebras es la ubicación relativa del grupo fosfato 5' terminal y el grupo hidroxilo 3' terminal (en los extremos de la hebra o secuencia en cuestión), porque estos extremos determinan la dirección de la transcripción y la traducción. Una secuencia escrita 5'-CGCTAT-3' es equivalente a una secuencia escrita 3'-TATCGC-5' siempre que se indiquen los extremos 5' y 3'. Si los extremos no están etiquetados, la convención es asumir que ambas secuencias están escritas en la dirección 5' a 3'. La "cadena Watson" se refiere a la cadena superior de 5' a 3' (5'→3'), mientras que la "cadena Crick" se refiere a la cadena inferior de 5' a 3' (3'←5'). Tanto la cadena Watson como la cadena Crick pueden ser cadenas con sentido o antisentido, dependiendo del producto genético específico que se obtenga de ellas.
Por ejemplo, la notación "YEL021W", un alias del gen URA3 utilizado en la base de datos del Centro Nacional de Información Biotecnológica (NCBI), indica que este gen se encuentra en el marco de lectura abierto (ORF) 21 desde el centrómero del brazo izquierdo (L) del cromosoma V (E) de la levadura (Y), y que la hebra codificante de expresión es la hebra Watson (W). "YKL074C" indica el marco de lectura abierto 74 a la izquierda del centrómero del cromosoma XI y que la hebra codificante es la hebra Crick (C). Otro término confuso que se refiere a las hebras "Plus" y "Minus" también se utiliza ampliamente. Ya sea que la hebra sea sentido (positiva) o antisentido (negativa), la secuencia de consulta predeterminada en la alineación NCBI BLAST es la hebra "Plus".
Ambisense
Un genoma monocatenario que se utiliza tanto en sentido positivo como negativo se denomina ambisense. Algunos virus tienen genomas ambisense. Los bunyavirus tienen tres fragmentos de ARN monocatenario (ssRNA), algunos de los cuales contienen secciones tanto de sentido positivo como de sentido negativo; los arenavirus también son virus ssRNA con un genoma ambisense, ya que tienen tres fragmentos que son principalmente de sentido negativo, excepto una parte de los extremos 5′ de los segmentos grande y pequeño de su genoma.
Antisense RNA
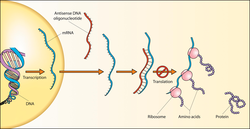
Una secuencia de ARN que es complementaria a una transcripción de ARNm endógeno se denomina a veces "ARN antisentido". En otras palabras, es una cadena no codificante complementaria a la secuencia codificante del ARN; esto es similar al ARN viral de sentido negativo. Cuando el ARNm forma un dúplex con una secuencia de ARN antisentido complementaria, se bloquea la traducción. Este proceso está relacionado con la interferencia del ARN. Las células pueden producir moléculas de ARN antisentido de forma natural, llamadas microARN, que interactúan con moléculas de ARNm complementarias e inhiben su expresión. El concepto también se ha explotado como una técnica de biología molecular, introduciendo artificialmente un transgén que codifica para el ARN antisentido con el fin de bloquear la expresión de un gen de interés. El ARN antisentido marcado radiactivamente o con fluorescencia se puede utilizar para mostrar el nivel de transcripción de genes en varios tipos de células.
Se han aplicado experimentalmente algunos tipos alternativos de estructuras antisentido como terapia antisentido. En los Estados Unidos, la Administración de Alimentos y Medicamentos (FDA) ha aprobado los oligonucleótidos antisentido fosforotioato fomivirsen (Vitravene) y mipomersen (Kynamro) para uso terapéutico en humanos.
Sentido del ARN en virus
En virología, el término "sentido" tiene un significado ligeramente diferente. Se puede decir que el genoma de un virus de ARN es de "sentido positivo", también conocido como "cadena positiva", o de "sentido negativo", también conocido como "cadena negativa". En la mayoría de los casos, los términos "sentido" y "cadena" se utilizan indistintamente, lo que hace que términos como "cadena positiva" sean equivalentes a "sentido positivo" y "cadena positiva" equivalentes a "sentido positivo". El hecho de que un genoma viral sea de sentido positivo o negativo se puede utilizar como base para clasificar los virus.
Sentido positivo
El ARN viral de sentido positivo (5′ a 3′) significa que una secuencia particular de ARN viral puede traducirse directamente en proteínas virales (por ejemplo, las necesarias para la replicación viral). Por lo tanto, en los virus de ARN de sentido positivo, el genoma de ARN viral puede considerarse ARNm viral y puede ser traducido inmediatamente por la célula huésped. A diferencia del ARN de sentido negativo, el ARN de sentido positivo tiene el mismo sentido que el ARNm. Algunos virus (por ejemplo, Coronaviridae) tienen genomas de sentido positivo que pueden actuar como ARNm y usarse directamente para sintetizar proteínas sin la ayuda de un intermediario de ARN complementario. Debido a esto, estos virus no necesitan tener una ARN polimerasa empaquetada en el virión: la ARN polimerasa será una de las primeras proteínas producidas por la célula huésped, ya que es necesaria para que se replique el genoma del virus.
Negativo.
El ARN viral de sentido negativo (3′ a 5′) es complementario al ARNm viral, por lo que una ARN polimerasa dependiente de ARN debe producir un ARN de sentido positivo a partir de él antes de la traducción. Al igual que el ADN, el ARN de sentido negativo tiene una secuencia de nucleótidos complementaria al ARNm que codifica; también, al igual que el ADN, este ARN no puede traducirse en proteínas directamente. En cambio, primero debe transcribirse en un ARN de sentido positivo que actúa como ARNm. Algunos virus (por ejemplo, los virus de la gripe) tienen genomas de sentido negativo y, por lo tanto, deben llevar una ARN polimerasa dentro del virión.
Antisense oligonucleótidos
El silenciamiento génico se puede lograr introduciendo en las células un oligonucleótido antisentido corto que sea complementario a un ARN diana. Este experimento fue realizado por primera vez por Zamecnik y Stephenson en 1978 y sigue siendo un enfoque útil, tanto para experimentos de laboratorio como para aplicaciones clínicas (terapia antisentido). Varios virus, como los virus de la gripe, el virus respiratorio sincitial (VRS) y el coronavirus del SARS (SARS-CoV), han sido atacados utilizando oligonucleótidos antisentido para inhibir su replicación en las células huésped.
Si el oligonucleótido antisentido contiene un tramo de ADN o un imitador de ADN (ADN fosforotioato, 2'F-ANA u otros), puede reclutar a la ARNasa H para degradar el ARN diana. Esto hace que el mecanismo de silenciamiento génico sea catalítico. El ARN bicatenario también puede actuar como un agente antisentido catalítico dependiente de enzimas a través de la vía ARNi/siRNA, que implica el reconocimiento del ARNm diana a través del apareamiento de cadenas con sentido y antisentido seguido de la degradación del ARNm diana por el complejo de silenciamiento inducido por ARN (RISC). El sistema hok/sok del plásmido R1 proporciona otro ejemplo más de un proceso de regulación antisentido dependiente de enzimas a través de la degradación enzimática del dúplex de ARN resultante.
Otros mecanismos antisentido no dependen de enzimas, sino que implican un bloqueo estérico de su ARN diana (por ejemplo, para evitar la traducción o inducir un empalme alternativo). Los mecanismos antisentido de bloqueo estérico suelen utilizar oligonucleótidos muy modificados. Dado que no es necesario el reconocimiento por la ARNasa H, esto puede incluir productos químicos como 2'-O-alquilo, ácido nucleico peptídico (PNA), ácido nucleico bloqueado (LNA) y oligómeros de morfolino.
Véase también
- Terapia antisense
- Dirección (biología molecular)
- DNA codon table
- Virus del ARN
- Transcripción (genética)
- Traducción (genética)
- Reproducción viral
Referencias
- ^ Anne-Lise Haenni (2003). "Estrategias de expresión de virus ambisenses". Virus Research. 93 (2): 141–150. doi:10.1016/S0168-1702(03)00094-7. PMID 12782362.
- ^ Kakutani T; Hayano Y; Hayashi T; Minobe Y. (1991). "Ambisense segmento 3 del virus de la raya de arroz: la primera instancia de un virus que contiene dos segmentos del ambiente". J Gen Virol. 72 (2): 465-8. doi:10.1099/0022-1317-72-2-465. PMID 1993885.
- ^ Zhu Y; Hayakawa T; Toriyama S; Takahashi M. (1991). "Secuencia completa de nucleótido del ARN 3 del virus de la raya de arroz: una estrategia de codificación ambisense". J Gen Virol. 72 (4): 763–7. doi:10.1099/0022-1317-72-4-763. PMID 2016591.
- ^ Cartwright, Reed; Dan Graur (Feb 8, 2011). "Las múltiples personalidades de Watson y las cadenas Crick". Biology Direct. 6: 7. doi:10.1186/1745-6150-6-7. PMC 3055211. PMID 21303550.
- ^ "FDA aprueba fomivirsen para CMV". healio. 1o de octubre de 1998. Retrieved 18 de septiembre 2020.
- ^ "FDA aprueba el medicamento huérfano para el trastorno hereditario del colesterol". Temas de drogas30 de enero de 2013. Retrieved 18 de septiembre 2020.
- ^ Zamecnik, P.C.; Stephenson, M.L. (1978). "Inhibición de la replicación del virus de Rous sarcoma y la transformación celular por un Oligodeoxynucleótido específico". Proc. Natl. Acad. Sci. USA. 75 (1): 280–284. Bibcode:1978PNAS...75..280Z doi:10.1073/pnas.75.1.280. PMC 411230. PMID 75545.
- ^ Watts, J.K.; Corey, D.R. (2012). "Silencing Disease Genes in the Laboratory and in the Clinic". J. Pathol. 226 (2): 365–379. doi:10.1002/path.2993. PMC 3916955. PMID 22069063.
- ^ a b c Kumar, Binod; Khanna, Madhu; Meseko, Clement A.; Sanicas, Melvin; Kumar, Prashant; Asha, Kumari; Asha, Kumari; Kumar, Prashant; Sanicas, Melvin (enero 2019). "Advancements in Nucleic Acid Based Therapeutics against Respiratory Viral Infections". Journal of Clinical Medicine. 8 (1): 6. doi:10.3390/jcm8010006. PMC 6351902. PMID 30577479.
- ^ Kumar, Binod; Asha, Kumari; Khanna, Madhu; Ronsard, Larance; Meseko, Clement Adebajo; Sanicas, Melvin (2018-01-10). "La amenaza emergente del virus de la gripe: estado y nuevas perspectivas para su terapia y control". Archivos de Virología. 163 (4): 831–844. doi:10.1007/s00705-018-3708-y. ISSN 0304-8608. PMC 7087104. PMID 29322273.
- ^ Kumar, Prashant; Kumar, Binod; Rajput, Roopali; Saxena, Latika; Banerjea, Akhil C.; Khanna, Madhu (2013-06-02). "Cross-Protective Effect of Antisense Oligonucleotide Developed Against the Common 3′ NCR of Influenza A Virus Genome". Biotecnología molecular. 55 (3): 203–211. doi:10.1007/s12033-013-9670-8. ISSN 1073-6085. PMID 23729285. S2CID 24496875.
- ^ Kumar, B.; Khanna, Madhu; Kumar, P. Sood, V.; Vyas, R.; Banerjea, A. C. (2011-07-09). "Nucleic Acid-Mediated Cleavage of M1 Gene of Influenza A Virus está significativamente aumentado por los moldes antisenses dirigidos a híbrido cerca del sitio Cleavage". Biotecnología molecular. 51 (1): 27–36. doi:10.1007/s12033-011-9437-z. ISSN 1073-6085. PMID 21744034. S2CID 45686564.