Proyecto del Microbioma Humano
Introducción
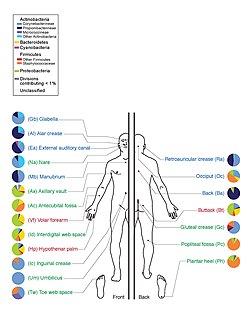
El HMP se ha descrito como "una extensión conceptual y experimental lógica del Proyecto Genoma Humano". En 2007, el HMP se incluyó en la Hoja de Ruta para la Investigación Médica de los NIH como una de las "Nuevas Vías para el Descubrimiento". La caracterización organizada del microbioma humano también se está realizando a nivel internacional bajo los auspicios del Consorcio Internacional del Microbioma Humano. Los Institutos Canadienses de Investigación en Salud, a través del Instituto de Infecciones e Inmunidad de los CIHR, lideran la Iniciativa Canadiense del Microbioma para desarrollar una iniciativa de investigación coordinada y enfocada en el análisis y la caracterización de los microbios que colonizan el cuerpo humano y su posible alteración durante las enfermedades crónicas.El HMP abordará algunas de las cuestiones científicas más inspiradoras, inquietantes y fundamentales de hoy. Importantemente, también tiene el potencial de romper las barreras artificiales entre la microbiología médica y la microbiología ambiental. Se espera que el HMP no solo identifique nuevas formas de determinar la salud y la predisposición a las enfermedades, sino que también defina los parámetros necesarios para diseñar, implementar y supervisar estrategias para manipular intencionalmente la microbiota humana, optimizar su rendimiento en el contexto de la fisiología de un individuo.
Instituciones contributivas
Fase 1 (2007-2014)
- Desarrollar un conjunto de referencia de secuencias de genoma microbiano y realizar caracterización preliminar del microbioma humano
- Explore la relación entre la enfermedad y los cambios en el microbioma humano
- Desarrollar nuevas tecnologías e instrumentos para el análisis computacional
- Establecer un repositorio de recursos
- Estudiar las implicaciones éticas, legales y sociales de la investigación del microbioma humano
Fase Dos (2014-2016)
El proyecto comprendió tres subproyectos realizados en diversas instituciones. Los métodos de estudio incluyeron el perfilado génico del ARNr 16S, la secuenciación shotgun del metagenoma completo, la secuenciación del genoma completo, la metatranscriptómica, la metabolómica/lipidómica y la inmunoproteómica. Los hallazgos clave del iHMP se publicaron en 2019.El iHMP creará conjuntos de datos longitudinales integrados de propiedades biológicas tanto del microbioma como del anfitrión de tres estudios de cohortes diferentes de las condiciones asociadas con microbiome utilizando múltiples tecnologías "omics".
Embarazo " Preterm Nacimiento
Comienzo de la enfermedad inflamatoria del intestino (IBD)
Inicio de la diabetes tipo 2 (T2D)
Logros
- Elaboración de nuevos sistemas de bases de datos que permitan una organización eficiente, almacenamiento, acceso, búsqueda y anotación de cantidades masivas de datos. Estos incluyen IMG, la base de datos de Genomes Microbiales Integrados y el sistema de análisis comparativo; IMG/M, un sistema relacionado que integra conjuntos de datos de metagenome con genomas microbianos aislados del sistema IMG; CharProtDB, una base de datos de anotaciones de proteínas experimentalmente caracterizadas; y la base de datos Genomes OnLine (GOLD), para monitorizar el estado de sus proyectos genómicos y metagenomicos asociados a todo el mundo.
- Elaboración de instrumentos para el análisis comparativo que faciliten el reconocimiento de patrones comunes, temas principales y tendencias en conjuntos complejos de datos. Estos incluyen RAPSearch2, una herramienta de búsqueda rápida y eficiente en memoria de datos de secuenciación de próxima generación; Boulder ALignment Editor (ALE), una herramienta de alineación RNA basada en la web; WebMGA, un servidor web personalizable para el análisis rápido de secuencias metagenómicas; y DNACLUST, una herramienta para la agrupación precisa y eficiente de genes marcador filogenético
- Desarrollo de nuevos métodos y sistemas para el montaje de conjuntos de datos de secuencia masiva. Ningún algoritmo de montaje único aborda todos los problemas conocidos de montaje secuencias de corta duración, por lo que los programas de montaje de próxima generación como AMOS son modulares, ofreciendo una amplia gama de herramientas para el montaje. Se han desarrollado algoritmos novedosos para mejorar la calidad y utilidad de las secuencias de los proyectos de genoma.
- Montaje de un catálogo de genomas de referencia secuenciados de cepas bacterianas puras de múltiples sitios corporales, contra los cuales se pueden comparar resultados metagenómicos. El objetivo original de 600 genomas ha sido muy superado; el objetivo actual es que 3.000 genomas estén en este catálogo de referencia, secuenciado al menos a un borrador de alta calidad. Hasta marzo de 2012, se han catalogado 742 genomas.
- Establecimiento del Centro de Análisis y Coordinación de Datos (DACC), que sirve de depósito central para todos los datos de HMP.
- Varios estudios que exploran cuestiones jurídicas y éticas relacionadas con la investigación de secuenciación del genoma entero.
- Nuevos métodos predictivos para identificar sitios de unión de factores de transcripción activos.
- Identificación, sobre la base de pruebas bioinformáticas, de un precursor de portador de electrones ampliamente distribuido y producido ribosomicamente
- Tiempo-lapso "imágenes de movimiento" del microbioma humano.
- Identificación de adaptaciones únicas adoptadas por bacterias filamentosas segmentadas (SFB) en su papel como comas intestinales. SFB son médicamente importantes porque estimulan las células T helper 17, pensado para jugar un papel clave en la enfermedad autoinmune.
- Identificación de factores que distinguen la microbiota del intestino sano y enfermo.
- Identificación de un rol dominante hasta ahora no reconocido de Verrucomicrobiota en comunidades bacterianas del suelo.
- Determinación de los factores que determinan el potencial de virulencia Gardnerella vaginalis cepas en vaginosis.
- Identificación de un vínculo entre la microbiota oral y la aterosclerosis.
- Demostración de especies patógenas Neisseria involucrada en meningitis, sepsis y enfermedad de transmisión sexual intercambian factores de virulencia con especies comunales.
Hitos
Base de datos de referencia establecida
- Los microbios aportan más genes responsables de la supervivencia humana que los propios genes humanos. Se estima que los genes bacterianos de codificación de proteínas son 360 veces más abundantes que los genes humanos.
- Actividades metabólicas microbianas; por ejemplo, la digestión de grasas; no siempre son proporcionadas por la misma especie bacteriana. La presencia de las actividades parece importar más.
- Los componentes del microbioma humano cambian con el tiempo, afectado por un estado de enfermedad paciente y medicamentos. Sin embargo, el microbioma finalmente regresa a un estado de equilibrio, aunque la composición de los tipos bacterianos ha cambiado.
Aplicación clínica
Aplicación farmacéutica
Véase también
- Microbiología ambiental
- Proyecto genoma
- Genómica
- Microbioma humano
- Gut flora
- Microbiología oral
- Flora de piel
- Flora vaginal
- Viroma humana
- Microbiología médica
- Metagenomics
- Ecología microbiana
- Microflora
- Organismo multigeo
- Superorganismo
Referencias
- ^ "Microbioma humano Proyecto: Diversidad de Microbios Humanos Más Grande que Predictado anteriormente". ScienceDaily. Retrieved 8 de marzo 2012.
- ^ "Proyecto de Microbioma Humana - Home ← Fondo Común NIH". commonfund.nih.gov28 de junio de 2013. Retrieved 2018-04-15.
- ^ "Human Microbiome Project". Fondo Común de la NIH. Retrieved 8 de marzo 2012.
- ^ a b American Academy of Microbiology FAQ: Human Microbiome Archived 2016-12-31 en la Wayback Machine enero 2014
- ^ Judá L. Rosner for Microbe Magazine, Feb 2014. ¿Diez veces más células microbianas que células corporales en humanos?
- ^ Alison Abbott for Nature News. Jan 8 2016 Los científicos mitaron que nuestros cuerpos tienen más bacterias que las células humanas
- ^ Sender R, Fuchs S, Milo R (enero 2016). "¿Estamos realmente superados en número? Revisiting the Ratio of Bacterial to Host Cells in Humans". Celular. 164 3): 337 –40. doi:10.1016/j.cell.2016.01.013. PMID 26824647.
- ^ a b Turnbaugh PJ, Ley RE, Hamady M, Fraser-Liggett CM, Knight R, Gordon JI (octubre de 2007). "El proyecto de microbioma humano". Naturaleza. 449 (7164): 804 –10. Bibcode:2007Natur.449..804T. doi:10.1038/nature06244. PMC 3709439. PMID 17943116.
- ^ "Sobre la hoja de ruta NIH". El Fondo Común NIH. Archivado desde el original el 17 de febrero de 2013. Retrieved 8 de marzo 2012.
- ^ "El Consorcio Internacional de Microbioma Humana". Retrieved 8 de marzo 2012.
- ^ "Iniciativa de Microbioma Canadiense". Canadian Institutes of Health Research. 13 August 2009. Retrieved 8 de marzo 2012.
- ^ "Human Microbiome Project / Funded Research". Fondo Común de la NIH. Retrieved 8 de marzo 2012.
- ^ "Proyecto de microbioma humano / Iniciativas de programas". El Fondo Común NIH. Archivado desde el original el 16 de noviembre de 2013. Retrieved 8 de marzo 2012.
- ^ a b "NH Proyecto Microbiome Humano - Sobre el Microbiome Humano". hmpdacc.org. Retrieved 2018-03-30.
- ^ NIH Equipo de Análisis de Portafolio Microbioma Humano (2019). "Una revisión de 10 años de actividades de investigación de microbioma humano en los Institutos Nacionales de Salud de los Estados Unidos, Ejercicios Fiscales 2007-2016". Microbioma. 7 1): 31. doi:10.1186/s40168-019-0620-y. ISSN 2049-2618. PMC 6391833. PMID 30808411.
- ^ Ferré C, Callaghan W, Olson C, Sharma A, Barfield W (noviembre 2016). "Efectos de la edad materna y tasas de nacimiento prematuros por edad en las tasas generales de nacimiento prematuro - Estados Unidos, 2007 y 2014". MMWR. Morbidity and Mortality Weekly Report. 65 (43): 1181–1184. doi:10.15585/mmwr.mm6543a1. PMID 27811841.
- ^ "Infant Mortality ← Salud Maternoinfantil ← Salud Reproductiva Silencio CDC". www.cdc.gov. 2018-01-02. Retrieved 2018-04-03.
- ^ Consorcio, VCU, Microbioma vaginal. "Vaginal Microbiome Consortium". vmc.vcu.edu. Retrieved 2018-04-05.
{{cite web}}: CS1 maint: múltiples nombres: lista de autores (link) - ^ "CDC - Epidemiología del IBD - Enfermedad Inflamatoria del Tazón". www.cdc.gov. Archivado desde el original en 2017-02-23. Retrieved 2018-04-15.
- ^ "Team". ibdmdb.org. Retrieved 2018-04-05.
- ^ "Informe Nacional de Estadísticas de Diabetes TENIDO Datos " Estadísticas TENIENDO Diabetes TENIDO CDC". www.cdc.gov. 2018-03-09. Retrieved 2018-04-15.
- ^ "Integrated Personal Omics Profiling sometida Integrated Personal Omics Profiling tención Stanford Medicine". med.stanford.edu. Retrieved 2018-04-05.
- ^ "Proyecto de Microbioma Humana - Home ← Fondo Común NIH". commonfund.nih.gov28 de junio de 2013. Retrieved 2019-04-18.
- ^ "Human Microbiome Project Data Portal". portal.hmpdacc.org. Retrieved 2019-04-18.
- ^ Markowitz VM, Chen IM, Palaniappan K, Chu K, Szeto E, Grechkin Y, Ratner A, Jacob B, Huang J, Williams P, Huntemann M, Anderson I, Mavromatis K, Ivanova NN, Kyrpides NC (enero de 2012). "IMG: la base de datos de microbios integrados y el sistema de análisis comparativo". Nucleic Acids Research. 40 (Problema de base): D115–22. doi:10.1093/nar/gkr1044. PMC 3245086. PMID 22194640.
- ^ Markowitz VM, Chen IM, Chu K, Szeto E, Palaniappan K, Grechkin Y, Ratner A, Jacob B, Pati A, Huntemann M, Liolios K, Pagani I, Anderson I, Mavromatis K, Ivanova NN, Kyrpides NC (enero de 2012). "IMG/M: el sistema integrado de gestión de datos de metagenome y análisis comparativo". Nucleic Acids Research. 40 (Díatabase issue): D123–9. doi:10.1093/nar/gkr975. PMC 3245048. PMID 22086953.
- ^ Madupu R, Richter A, Dodson RJ, Brinkac L, Harkins D, Durkin S, Shrivastava S, Sutton G, Haft D (enero de 2012). "CharProtDB: una base de datos de anotaciones de proteínas caracterizadas experimentalmente". Nucleic Acids Research. 40 (Problema de datos): D237–41. doi:10.1093/nar/gkr1133. PMC 3245046. PMID 22140108.
- ^ Pagani I, Liolios K, Jansson J, Chen IM, Smirnova T, Nosrat B, Markowitz VM, Kyrpides NC (enero de 2012). "The Genomes OnLine Database (GOLD) v.4: status of genomic and metagenomic projects and their associated metadata". Nucleic Acids Research. 40 (Tema de la base de datos): D571–9. doi:10.1093/nar/gkr1100. PMC 3245063. PMID 22135293.
- ^ Zhao Y, Tang H, Ye Y (enero de 2012). "RAPSearch2: una herramienta de búsqueda rápida y eficiente en memoria para datos de secuenciación de próxima generación". Bioinformática. 28 1): 125–6. doi:10.1093/bioinformática/btr595. PMC 3244761. PMID 22039206.
- ^ Stombaugh J, Widmann J, McDonald D, Knight R (junio de 2011). "Boulder ALignment Editor (ALE): una herramienta de alineación RNA basada en web". Bioinformática. 27 (12): 1706 –7. doi:10.1093/bioinformática/btr258. PMC 3106197. PMID 21546392.
- ^ Wu S, Zhu Z, Fu L, Niu B, Li W (septiembre 2011). "WebMGA: un servidor web personalizable para el análisis rápido de secuencia metagenomic". BMC Genomics. 12: 444. doi:10.1186/1471-2164-12-444. PMC 3180703. PMID 21899761.
- ^ Ghodsi M, Liu B, Pop M (junio de 2011). "DNACLUST: agrupación precisa y eficiente de genes marcadores filogenéticos". BMC Bioinformática. 12: 271. doi:10.1186/1471-2105-12-271. PMC 3213679. PMID 21718538.
- ^ Yao G, Ye L, Gao H, Minx P, Warren WC, Weinstock GM (enero de 2012). "Conforme gráfico de las asambleas secuenciales de próxima generación". Bioinformática. 28 1): 13 –6. doi:10.1093/bioinformática/btr588. PMC 3244760. PMID 22025481.
- ^ Treangen TJ, Sommer DD, Angly FE, Koren S, Pop M (marzo 2011). Secuencia de próxima generación montaje con AMOS. Vol. Chapter 11. pp. Unit 11.8. doi:10.1002/0471250953.bi1108s33. ISBN 978-0471250951. PMC 3072823. PMID 21400694.
{{cite book}}:|journal=ignorado (ayuda) - ^ Koren S, Miller JR, Walenz BP, Sutton G (septiembre de 2010). "Un algoritmo para el cierre automatizado durante el montaje". BMC Bioinformática. 11: 457. doi:10.1186/1471-2105-11-457. PMC 2945939. PMID 20831800.
- ^ "Human Microbiome Project / Referencia Genomes Data". Data Analysis and Coordination Center (DACC) for the National Institutes of Health (NIH). Retrieved 8 de marzo 2012.
- ^ "Data Analysis and Coordination Center (DACC)". National Institutes of Health (NIH) Fondo Común. Retrieved 11 de marzo 2012.
- ^ Schwab AP, Frank L, Gligorov N (noviembre de 2011). "Guardar privacidad, significa confidencialidad". El American Journal of Bioethics. 11 (11): 44 –5. doi:10.1080/15265161.2011.608243. PMID 22047127. S2CID 34313782.
- ^ Rhodes R, Azzouni J, Baumrin SB, Benkov K, Blaser MJ, Brenner B, Dauben JW, Earle WJ, Frank L, Gligorov N, Goldfarb J, Hirschhorn K, Hirschhorn R, Holzman I, Indyk D, Jabs EW, Lackey DP, Moros DA, Philpott S, Rhodes "De minimis risk: a proposal for a new category of research risk". El American Journal of Bioethics. 11 (11): 1 –7. doi:10.1080/15265161.2011.615588. PMID 22047112. S2CID 205859554.
- ^ McGuire AL, Lupski JR (mayo de 2010). "Investigación del genoma personal: ¿qué debe decir el participante?". Tendencias en la genética. 26 5): 199 –201. doi:10.1016/j.tig.2009.12.007. PMC 2868334. PMID 20381895.
- ^ Sharp RR, Achkar JP, Brinich MA, Farrell RM (abril de 2009). "Los pacientes que buscan tomar decisiones informadas sobre los probióticos: una necesidad de investigación". El American Journal of Gastroenterology. 104 4): 809 –13. doi:10.1038/ajg.2008.68. PMC 2746707. PMID 19343022.
- ^ Cuellar-Partida G, Buske FA, McLeay RC, Whitington T, Noble WS, Bailey TL (enero de 2012). "Epigenetic priors for identifying active transcription factor binding sites". Bioinformática. 28 1): 56 –62. doi:10.1093/bioinformática/btr614. PMC 3244768. PMID 22072382.
- ^ Haft DH (enero de 2011). "Evidencia bioinformática para un precursor de portador de electrones ampliamente distribuido y producido ribosomicamente, sus proteínas de maduración y sus socios de redox nicotinoproteína". BMC Genomics. 12: 21. doi:10.1186/1471-2164-12-21. PMC 3023750. PMID 21223593.
- ^ Caporaso JG, Lauber CL, Costello EK, Berg-Lyons D, Gonzalez A, Stombaugh J, Knights D, Gajer P, Ravel J, Fierer N, Gordon JI, Knight R (2011). "Moving pictures of the human microbiome". Génova Biología. 12 (5): R50. doi:10.1186/gb-2011-12-5-r50. PMC 3271711. PMID 21624126.
- ^ Sczesnak A, Segata N, Qin X, Gevers D, Petrosino JF, Huttenhower C, Littman DR, Ivanov II (septiembre 2011). "El genoma de las bacterias filamentosas segmentadas que inducen células th17 revela una auxotrofia extensa y adaptaciones al entorno intestinal". Cell Host & Microbe. 10 3): 260 –72. doi:10.1016/j.chom.2011.08.005. PMC 3209701. PMID 21925113.
- ^ Ballal SA, Gallini CA, Segata N, Huttenhower C, Garrett WS (abril de 2011). "factores simbióticos de microbiota caliente y intestinal: lecciones de la enfermedad inflamatoria intestinal y simbientes exitosos". Microbiología celular. 13 4): 508 –17. doi:10.1111/j.1462-5822.2011.01572.x. PMID 21314883. S2CID 205529660.
- ^ Bergmann GT, Bates ST, Eilers KG, Lauber CL, Caporaso JG, Walters WA, Knight R, Fierer N (Julio 2011). "La dominación sub-reconocida de Verrucomicrobia en comunidades bacterianas del suelo". Biología del suelo " Bioquímica ". 43 (7): 1450 –1455. Bibcode:2011SBi...43.1450B. doi:10.1016/j.soilbio.2011.03.012. PMC 3260529. PMID 22267877.
- ^ Yeoman CJ, Yildirim S, Thomas SM, Durkin AS, Torralba M, Sutton G, Buhay CJ, Ding Y, Dugan-Rocha SP, Muzny DM, Qin X, Gibbs RA, Leigh SR, Stumpf R, White BA, Highlander SK, Nelson KE, Wilson BA (agosto de 2010). Li W (ed.). "La genómica comparativa de las cepas de Gardnerella vaginalis revela diferencias sustanciales en el potencial metabólico y virulencia". PLOS ONE. 5 (8): e12411. Bibcode:2010PLoSO...512411Y. doi:10.1371/journal.pone.0012411. PMC 2928729. PMID 20865041.
- ^ Koren O, Spor A, Felin J, Fåk F, Stombaugh J, Tremaroli V, Behre CJ, Knight R, Fagerberg B, Ley RE, Bäckhed F (Marzo 2011). "Microbiota humana oral, intestinal y placa en pacientes con aterosclerosis". Actas de la Academia Nacional de Ciencias de los Estados Unidos de América. 108 Suppl 1 (Suplemento_1): 4592 –8. Bibcode:2011PNAS..108.4592K doi:10.1073/pnas.1011383107. PMC 3063583. PMID 20937873.
- ^ Marri PR, Paniscus M, Weyand NJ, Rendón MA, Calton CM, Hernández DR, Higashi DL, Sodergren E, Weinstock GM, Rounsley SD, So M (Julio 2010). Ahmed N (ed.). "La secuenciación del genoma revela un amplio intercambio de genes de virulencia entre las especies humanas de Neisseria". PLOS ONE. 5 (7): e11835. Bibcode:2010PLoSO...511835M. doi:10.1371/journal.pone.0011835. PMC 2911385. PMID 20676376.
- ^ a b "NH Human Microbiome Project define el maquillaje bacteriano normal del cuerpo". NIH News. 13 de junio de 2012.
- ^ Human Microbiome Project Consortium (junio de 2012). "Un marco para la investigación de microbioma humano". Naturaleza. 486 (7402): 215–21. Bibcode:2012Natur.486..215T. doi:10.1038/nature11209. PMC 3377744. PMID 22699610.
- ^ Human Microbiome Project Consortium (junio de 2012). "Strutura, función y diversidad del microbioma humano sano". Naturaleza. 486 (7402): 207–14. Bibcode:2012Natur.486..207T. doi:10.1038/nature11234. PMC 3564958. PMID 22699609.
- ^ Cantarel BL, Lombard V, Henrissat B (2012). "La utilización de carbohidratos complejos por el microbioma humano saludable". PLOS ONE. 7 (6): e28742. Código:2012PLoSO...728742C. doi:10.1371/journal.pone.0028742. PMC 3374616. PMID 22719820.
- ^ Wu YW, Rho M, Doak TG, Ye Y (agosto 2012). "Las espiroquetas orales implicadas en enfermedades dentales están generalizadas en sujetos humanos normales y llevan cassettes genéticas de integrón muy diversas". Microbiología aplicada y ambiental. 78 (15): 5288–96. Bibcode:2012ApEnM..78.5288W. doi:10.1128/AEM.00564-12. PMC 3416431. PMID 22635997.
- ^ "PLOS Collections: colecciones de artículos publicadas por la Biblioteca Pública de Ciencia". collections.plos.org. Retrieved 2018-04-15.
- ^ "Summaries Manuscritos" (PDF). Archivado desde el original (PDF) on 2014-03-04. Retrieved 2012-11-06.
- ^ Wilder, C, Sandle T, Sutton S (junio 2013). "Implicaciones del Microbioma Humano en Microbiología Farmacéutica". American Pharmaceutical Review.
Enlaces externos
- Microbioma humano Proyecto
- Data Analysis and Coordination Center for the Human Microbiome Project (HMP)
- The CIHR Canadian Microbiome Initiative
- El Consorcio Internacional de Microbioma Humana
- 2006, Resumen de estudio de microbioma de colon (el estudio real: Gill et al., 2006)
- Olivia Judson Microbes ‘R’ Nosotros Archivado 2009-09-27 en la máquina Wayback New York Times 22 de julio de 2009
- Gina Kolata ¿Buena salud? Gracias a sus 100 bacterias Trillion New York Times 13 de junio de 2012