Gráficos moleculares
Los gráficos moleculares son la disciplina y filosofía que estudia las moléculas y sus propiedades mediante representaciones gráficas. La IUPAC limita la definición a las representaciones en un "dispositivo de visualización gráfica". Desde los átomos de Dalton y el benceno de Kekulé, ha habido una rica historia de átomos y moléculas dibujados a mano, y estas representaciones han tenido una influencia importante en los gráficos moleculares modernos.
Los gráficos moleculares en color se utilizan a menudo en las portadas de revistas de química con fines artísticos.
Historia
Antes de que se utilizaran gráficos de computadora para representar la estructura molecular, Robert Corey y Linus Pauling desarrollaron un sistema para representar átomos o grupos de átomos de madera dura en una escala de 1 pulgada = 1 angstrom conectados por un dispositivo de sujeción para mantener la configuración molecular. Estos primeros modelos también establecieron el esquema de coloración CPK que todavía se utiliza hoy en día para diferenciar los diferentes tipos de átomos en los modelos moleculares (por ejemplo, carbono = negro, oxígeno = rojo, nitrógeno = azul, etc.). Este modelo inicial fue mejorado en 1966 por W.L. Koltun y ahora se conocen como modelos Corey-Pauling-Koltun (CPK).
Los primeros intentos de producir modelos de estructura molecular fueron realizados por el Proyecto MAC, utilizando modelos de estructura alámbrica que se mostraban en un tubo de rayos catódicos a mediados de los años 60. En 1965, Carroll Johnson distribuyó el gráfico de elipsoide térmico de Oak Ridge (ORTEP), que visualizaba las moléculas como un modelo de esferas y barras con líneas que representaban los enlaces entre átomos y elipsoides para representar la probabilidad de movimiento térmico. Los gráficos de elipsoide térmico se convirtieron rápidamente en el estándar de facto utilizado en la visualización de datos de cristalografía de rayos X, y todavía se utilizan ampliamente en la actualidad. El primer uso práctico de los gráficos moleculares fue una simple visualización de la proteína mioglobina utilizando una representación de estructura alámbrica en 1966 por Cyrus Levinthal y Robert Langridge, que trabajaban en el Proyecto MAC.
Entre los hitos de los gráficos moleculares de alto rendimiento se encuentra el trabajo de Nelson Max en la representación "realista" de macromoléculas utilizando esferas reflectantes.

Al principio, gran parte de la tecnología se centraba en los gráficos 3D de alto rendimiento. Durante la década de 1970, se desarrollaron métodos para mostrar gráficos 3D mediante tubos de rayos catódicos utilizando gráficos informáticos de tono continuo en combinación con dispositivos de visualización con obturador electroóptico. Los primeros dispositivos utilizaban un sistema 3D de obturador activo, que generaba diferentes vistas en perspectiva para el canal izquierdo y derecho para proporcionar la ilusión de una visión tridimensional. Las gafas de visión estereoscópica se diseñaron utilizando cerámica de titanato de zirconato de plomo y lantano (PLZT) como elementos de obturador controlados electrónicamente. Las gafas 3D activas requieren pilas y funcionan en conjunto con la pantalla para cambiar activamente la presentación de las lentes a los ojos del usuario. Muchas gafas 3D modernas utilizan un sistema 3D pasivo y polarizado que permite al usuario visualizar efectos 3D en función de su propia percepción. Las gafas 3D pasivas son más comunes hoy en día, ya que son menos costosas.
Los requisitos de la cristalografía macromolecular también impulsaron los gráficos moleculares porque las técnicas tradicionales de construcción de modelos físicos no podían escalarse. Las dos primeras estructuras de proteínas resueltas mediante gráficos moleculares sin la ayuda de la Caja de Richards se construyeron con el programa FIT de Stan Swanson en la pantalla de gráficos Vector General en el laboratorio de Edgar Meyer en la Universidad Texas A&M: primero Marge Legg en el laboratorio de Al Cotton en A&M resolvió una segunda estructura de mayor resolución de la nucleasa de estafilococo (1975) y luego Jim Hogle resolvió la estructura de la lisozima monoclínica en 1976. Pasó un año completo antes de que se utilizaran otros sistemas de gráficos para reemplazar la Caja de Richards para modelar la densidad en 3-D. El programa FRODO de Alwyn Jones (y más tarde "O") se desarrollaron para superponer la densidad electrónica molecular determinada a partir de la cristalografía de rayos X y la estructura molecular hipotética.
Timeline
| Desarrollado(s) | Fecha aproximada | Tecnología | Comentarios |
|---|---|---|---|
| Crystallographers | ▪ 1960 | Tirado a mano | Estructuras de cristal, con átomo oculto y eliminación de lazos. A menudo proyecciones clinográficas. |
| Johnson, madre. | c.1970 | Pen plotter | ORTEP, PLUTO. Muy ampliamente desplegado para la publicación de estructuras de cristal. |
| Cyrus Levinthal, Bob Langridge, Ward, Stots | 1966 | Proyecto MAC sistema de visualización, dos grados de libertad, muelle de velocidad de retorno para girar la imagen. | Primera pantalla de proteínas en pantalla. Sistema para la construcción interactiva de estructuras de proteínas. |
| Barry | 1969 | Computador LINC 300 con una pantalla de osciloscopio dual. | Sistema de visualización de la estructura molecular interactiva. Ejemplos tempranos de rotación dinámica, profundidad de intensidad·cate y estéreo lateral a lado. Uso temprano de las aproximaciones de ángulo pequeño (a = pecado a, 1 = por a) para acelerar los cálculos de rotación gráfica. |
| Ortony | 1971 | Diseñado un visor estéreo (British patent appl. 13844/70) para gráficos de computadora molecular. | El espejo horizontal de dos vías (half-silvered) combina imágenes dibujadas en las mitades superiores e inferiores de una TRC. Los polarizadores cruzados aíslan las imágenes a cada ojo. |
| Ortony | 1971 | Bolígrafo ligero, cangrejo. | Sistema de visualización de la estructura molecular interactiva. Seleccione el enlace girando otro botón hasta que el vínculo deseado se encienda en secuencia, una técnica más tarde utilizada en el sistema MMS-4 abajo, o seleccionando con el lápiz de luz. Los puntos en el espacio se especifican con un "bug" 3-D bajo control dinámico. |
| Barry, Graesser, Marshall | 1971 | CHEMAST: El ordenador LINC 300 conduce un osciloscopio. Joystick de dos ejes, similar a uno usado más adelante por GRIP-75 (bajo). | Sistema de visualización de la estructura molecular interactiva. Estructuras giradas dinámicamente utilizando el joystick. |
| Tountas y Katz | 1971 | Adage AGT/50 display | Sistema de visualización de la estructura molecular interactiva. Matemáticas de rotación anidada y de rotación de laboratorio-espacio. |
| Perkins, Piper, Tattam, White | 1971 | Honeywell DDP 516 ordenador, EAL TR48 ordenador analógico, osciloscopio Lanelec, 7 potenciómetros lineales. Stereo. | Sistema de visualización de la estructura molecular interactiva. |
| Wright | 1972 | GRIP-71 en UNC-CH: IBM System/360 Model 40 time-shared computer, IBM 2250 display, botones, lápiz ligero, teclado. | Manipulación discreta y relajación energética de las estructuras de proteínas. El código del programa se convirtió en la base del sistema GRIP-75 a continuación. |
| Barry and North | 1972 | Universidad de Oxford: Ferranti Argus 500 ordenador, Ferranti modelo 30 pantalla, teclado, pista bola, un botón. Stereo. | Sistema de solución cristalográfica de gran molécula. La bola de pista gira un enlace, el botón ilumina la molécula vs. mapa de densidad de electrones. |
| North, Ford, Watson | Principios de 1970 | Universidad de Leeds: DEC PDP·11/40 ordenador, pantalla Hewlett-Packard. 16 botones, teclado, joystick de retorno de primavera. Stereo. | Sistema de solución cristalográfica de gran molécula. Seis nubos rotan y traducen una pequeña molécula. |
| Barry, Bosshard, Ellis, Marshall, Fritch, Jacobi | 1974 | MMS-4: Universidad de Washington en St. Louis, ordenador LINC 300 y pantalla LDS-1 / LINC 300, módulos de visualización personalizados. Rotación joystick, pomos. Stereo. | Sistema de solución cristalográfica de gran molécula. Seleccione el enlace para rotar girando otro botón hasta que el enlace deseado se encienda en secuencia. |
| Cohen y Feldmann | 1974 | DEC PDP-10 ordenador, Pantalla de entrada, botones de empuje, teclado, botones | Sistema de solución cristalográfica de gran molécula. |
| Stellman | 1975 | Princeton University: ordenador PDP-10, pantalla LDS-1, pomos | Sistema de solución cristalográfica de gran molécula. Mapa de densidad de electrones no se muestra; en lugar de una figura de mérito "H Factor" se actualiza como la estructura molecular se manipula. |
| Collins, Cotton, Hazen, Meyer, Morimoto | 1975 | CRYSNET, Texas A plagaM Univ. DEC PDP-11/40 ordenador, Vector General Serie 3 pantalla, botones, teclado. Stereo. | Sistema de solución cristalográfica de gran molécula. Variedad de modos de visualización: rocking, spinning y varios modos de visualización estéreo. |
| Cornelius y Kraut | 1976 (aprox.) | University of California at San Diego: DEC PDP-11/40 emulator (CalData 135), Evans y Sutherland Picture System display, teclado, 6 cubos. Stereo. | Sistema de solución cristalográfica de gran molécula. |
| (Yale Univ.) | 1976 (aprox.) | PIGS: DEC PDP-11/70 ordenador, Evans y Sutherland Picture System 2 display, data tablet, pomos. | Sistema de solución cristalográfica de gran molécula. La tableta fue utilizada para la mayoría de las interacciones. |
| Feldmann y Porter | 1976 | NIH: DEC PDP-11/70 computer. Evans y Sutherland Picture System 2 pantalla, pomos. Stereo. | Sistema de visualización de la estructura molecular interactiva. Intended to display interactively molecular data from the AMSOM – Atlas of Macromolecular Structure on Microfiche. |
| Rosenberger et al. | 1976 | MMS-X: Universidad de Washington en St. Louis, ordenador TI 980B, Hewlett-Packard 1321A display, terminal de video Beehive, módulos de visualización personalizados, par de joysticks de retorno de resorte 3-D, pomos. | Prototipo (y posterior exitoso) sistema de solución cristalográfica de gran molécula. Sucesor del sistema MMS-4 arriba. Los joysticks de retorno de resorte 3-D traducen y giran la estructura molecular para ver o una subestructura molecular para el ajuste, modo controlado por un interruptor de toggle. |
| Britton, Lipscomb, Pique, Wright, Brooks | 1977 | GRIP-75 en UNC-CH: Time-shared IBM System/360 Model 75 computer, DEC PDP 11/45 computer, Vector General Series 3 display, 3-D movement box from A.M. Noll and 3-D spring return joystick for substructure manipulation, Medi Systems nested joystick, knobs, sliders, buttons, keyboard, light pen. | Primera solución cristalográfica de gran molécula. |
| Jones | 1978 | FRODO y RING Max Planck Inst., Alemania, RING: DEC PDP-11/40 y Siemens 4004 computadoras, Vector General 3404 pantalla, 6 botones. | Solución de estructura cristalográfica de gran molécula. FRODO puede haber corrido en un DEC VAX-780 como un seguimiento a RING. |
| Diamante | 1978 | Bilder Cambridge, Inglaterra, DEC PDP-11/50 ordenador, Evans y Sutherland Picture System display, tablet. | Solución de estructura cristalográfica de gran molécula. Toda la entrada es por la tableta de datos. Estructuras moleculares construidas en línea con geometría ideal. Más tarde pasa los lazos estirados con idealización. |
| Langridge, White, Marshall | A finales de 1970 | Sistemas departamentales (PDP-11, pantallas Tektronix o DEC-VT11, por ejemplo MMS-X) | Mezcla de cálculo de productos básicos con pantallas tempranas. |
| Davies, Hubbard | Mid-1980s | CHEM-X, HYDRA | Sistemas de laboratorio con dispositivos multicolores, raster y vectoriales (Sigmex, PS300). |
| Biosym, Tripos, Polygen | Mid-1980s | PS300 y terminales mudas de menor costo (VT200, SIGMEX) | Paquetes de modelado y visualización integrados comerciales. |
| Gráficos de silicona, Sol | A finales de 1980 | Estaciones de trabajo IRIS GL (UNIX) | Estaciones de trabajo de usuario único con precio de productos básicos con pantalla estereoscópica. |
| EMBL - Lo que si | 1989, 2000 | Máquina independiente | Casi gratis, multifuncional, todavía totalmente compatible, muchos servidores gratuitos basados en él |
| Sayle, Richardson | 1992, 1993 | RasMol, Kinemage | Plataforma independiente MG. |
| MDL (van Vliet, Maffett, Adler, Holt) | 1995-1998 | Chime | propietario C++; plugin de navegador gratuito para Mac (OS9) y PCs |
| MolSoft | 1997–presente | ICM-Browser | propietario; descarga gratuita para Windows, Mac y Linux. |
| 1998- | MarvinSketch " MarvinView. MarvinSpace (2005) | propietario Aplicación Java applet o independiente. |
Tipos
Modelos de bolas y palillos
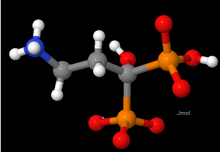
En el modelo de esferas y barras, los átomos se dibujan como pequeñas esferas conectadas por barras que representan los enlaces químicos entre ellas.
Modelos de relleno de espacio
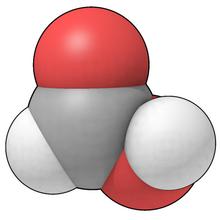
En el modelo de relleno de espacio, los átomos se dibujan como esferas sólidas para sugerir el espacio que ocupan, en proporción a sus radios de van der Waals. Los átomos que comparten un enlace se superponen entre sí.
Superficies

En algunos modelos, la superficie de la molécula se aproxima y se sombrea para representar una propiedad física de la molécula, como la densidad de carga electrónica.
Diagramas de cinta

Los diagramas de cinta son representaciones esquemáticas de la estructura de las proteínas y son uno de los métodos más comunes de representación de proteínas que se utilizan en la actualidad. La cinta muestra la ruta general y la organización de la estructura principal de la proteína en 3D y sirve como un marco visual en el que colgar detalles de la estructura atómica completa, como las bolas para los átomos de oxígeno unidos al sitio activo de la mioglobina en la imagen adyacente. Los diagramas de cinta se generan interpolando una curva suave a través de la estructura principal del polipéptido. Las hélices α se muestran como cintas enrolladas o tubos gruesos, las hebras β como flechas y las espirales o bucles no repetitivos como líneas o tubos delgados. La dirección de la cadena polipeptídica se muestra localmente mediante las flechas y puede indicarse en general mediante una rampa de color a lo largo de la cinta.
Véase también
- Modelo molecular
- Modelado molecular
- Geometría molecular
- Molecule editor
- Software
- Software gráfico molecular
- Software de modelado mecánico molecular
- Software de diseño molecular
Referencias
- ^ Dickerson, R.E.; Geis, I. (1969). La estructura y acción de las proteínas. Menlo Park, CA: W.A. Benjamin.
- ^ IUPAC, Compendio de Terminología Química, 2a edición. (el "Gold Book") (1997). Versión corregida online: (1997) "imágenes moleculares". doi:10.1351/goldbook.MT06970
- ^ Harrison, Karl; Bowen, Jonathan P.; Bowen, Alice M. (2013). Ng, Kia; Bowen, Jonathan P.; McDaid, Sarah (eds.). "La visualización electrónica en química: de la alquimia al arte". EVA London 2013 Activos de conferencias. Talleres electrónicos en Computing. British Computer Society. pp. 267–274.
- ^ Corey, Robert B.; Pauling, Linus (1953). "Moleculares Modelos de Aminoácidos, Peptidos y Proteínas". Examen de los instrumentos científicos. 24 (8): 621. Bibcode:1953RScI...24..621C doi:10.1063/1.1770803. Retrieved 13 de junio 2022.
- ^ Koltun, Walter L. (diciembre de 1965). "Modelos atómicos de relleno espacial de precisión". Biopolímeros. 3 (6): 665–679. doi:10.1002/bip.360030606. PMID 4158989. S2CID 38806627.
- ^ a b Atwood, Jerry L.; Barbour, Leonard J. (2003). "Gráficos moleculares: de la ciencia al arte". Crecimiento de cristal y diseño. 3 1): 3 a 8 doi:10.1021/cg020063o. Retrieved 13 de junio 2022.
- ^ Francoeur, Eric (2002). "Cyrus Levinthal, el Kluge y los orígenes de los gráficos moleculares interactivos". Endeavour. 26 (4): 127–131. doi:10.1016/S0160-9327(02)01468-0. PMID 12535918. Retrieved 13 de junio 2022.
- ^ Porter TK (agosto de 1978). "Spherical shading". ACM SIGGRAPH Computer Graphics. 12 (3): 282-5. doi:10.1145/965139.639789.
- ^ Ortonía, A. (mayo de 1971). "Un sistema de visualización de Stereo". The Computer Journal. 14 (2): 140-4. doi:10.1093/comjnl/14.2.140. También aparece en: Conferencia en pantallas, Institución de Ingenieros Eléctricos Conf. Pub. No. 80 (7 a 10 de septiembre de 1971), C. Baldwin Ltd., 225-232.
- ^ Roese, John A.; McCleary, Lawrence E. (agosto de 1979). "Gráficos de computación estereoscópicos para la simulación y modelación". ACM SIGGRAPH Computer Graphics. 13 (2): 41–47. doi:10.1145/965103.807423. Retrieved 14 de junio 2022.
- ^ Wiley, Suzanne S. (12 de mayo de 2022). "¿Qué son los vidrios 3D pasivos?". EasyTechJunkie. Retrieved 14 de junio 2022.
- ^ Levinthal, C. (junio 1966). "Molecular Model-building by Computer". Scientific American. 214 (6): 42–52. Bibcode:1966SciAm.214f..42L. doi:10.1038/cientificamerican0666-42. PMID 5930597.
- ^ Barry, C. D., Ellis, R. A., Graesser, S. M. y Marshall, G. R. 1969. Pantalla y manipulación en tres dimensiones. Pertinent Comcepts in Computer GraphicsUniv. de Ill. Prensa, 104-153.
- ^ Ortonía, A. 1971b. Estareografías interactivas Conferencia en pantallas, Institución de Ingenieros Eléctricos Conf. Pub. No. 80 (7-10 septiembre), C. Baldwin Ltd., 185-193.
- ^ Barry, C. D., Ellis, R. A., Graesser, S. M. y Marshall, G. R. 1971. CHEMAST: Programa informático para modelar estructuras moleculares. C. 1971 IFIP1552-1558.
- ^ Tountas, C. y Katz, L. 1971. Gráficos interactivos en biología molecular. Rotaciones tridimensionales en tiempo real de imágenes y fragmentos de imagen. Proc. Summer Computer Simulation Conf., 1, 241-247.
- ^ Perkins, W.J.; Piper, E.A.; Tattam, F.G.; White, J.C. (Junio 1971). "Computadoras estereoscópicas interactivas para investigación biomédica". Computadoras e Investigación Biomédica. 4 (3): 249–261. doi:10.1016/0010-4809(71)90030-9. PMID 5562569.
- ^ Wright, W. V. 1972a. Sistema Gráfico de Computación Interactiva para Estudios Moleculares. PhD Dissertation, University of North Carolina, Chapel Hill, North Carolina.
- ^ Wright, W.V. (octubre de 1972). "La interfaz bidimensional de un sistema interactivo para estudios moleculares". ACM SIGPLAN Avisos. 7 (10): 76–85. doi:10.1145/942576.807017.
- ^ a b Brooks FP Jr. The Computer "Scientist" as Toolsmith: Studies in Interactive Computer Graphics. Proc. IFIP, 625-634 (1977).
- ^ Barry CD, North AC (1972). "El uso de un sistema de visualización controlado por ordenador en el estudio de las conformaciones moleculares". Coño de primavera frío. Biol. 36: 577–84. doi:10.1101/SQB.1972.036.01.072. PMID 4508170.
- ^ Barry CD, Bosshard HE, Ellis RA, Marshall GR (diciembre de 1974). "Evolving macromodular molecular modeling system". Fed. Proc. 33 (12): 2368–72. PMID 4435239.
- ^ Fritch, J. M., Ellis, R. A., Jacobi T. H. y Marshall, G. R. 1975. Un sistema de gráficos macromoleculares para investigación de estructuras de proteínas. Computadoras y Gráficos, 1, #2/3 (septiembre), 271-278.
- ^ Cohen, G. H. and Feldmann, R. J. 1974. MAP - Programa de Computación Gráficos Interactivos para la Manipulación y Fitting de Molecules Protein a Mapas de Densidad Electron. Am. Crystallography. Assoc. Spring 23, (Abstr.).
- ^ Stellman, S.D. (septiembre de 1975). "Aplicación de gráficos interactivos tridimensionales en el análisis cristalinográfico de rayos X". Computadoras & Gráficos. 1 (2–3): 279–288. doi:10.1016/0097-8493(75)90019-9.
- ^ Collins DM, Cotton FA, Hazen EE, Meyer EF, Morimoto CN (diciembre de 1975). "Proteínas de cristal: enfoques más rápidos y más baratos". Ciencia. 190 (4219): 1047–53. Bibcode:1975 Sci...190.1047C. doi:10.1126/science.1188383. PMID 1188383. S2CID 44583219.
- ^ Feldmann, R. J. 1976. AMSOM – Atlas de la estructura macromolecular en microfiche.. Maryland: Tracor Jitco Inc.
- ^ Rosenberger, F. U., et al. 1976. Extracts from 1976 NIH Annual Report. Memorando técnico No 230, Laboratorio de Sistemas Informáticos, Universidad de Washington en St. Louis, Missouri.
- ^ Lipscomb, JS. Cues tridimensionales para un sistema de gráficos de computadora molecular. PhD Dissertation, University of North Carolina at Chapel Hill, North Carolina. (1981)
- ^ Britton E, Lipscomb JS, Pique ME, Wright, WV, Brooks FP Jr, Pique ME. The GRIP-75 Man-machine Interface. ACM SIGGRAPH Revisión de vídeo, (4), (Ago. 1981).
- ^ Britton, E. G. 1977. Metodología para el diseño ergonómico de sistemas de gráficos interactivos y su aplicación a la cristalografía. PhD Dissertation, University of North Carolina, Chapel Hill, North Carolina.
- ^ Pique, M. E. 1980. Rotaciones dinámicas anidadas para gráficos informáticos. M. S. Thesis, University of North Carolina, Chapel Hill, North Carolina.
- ^ Tsernoglou D, Petsko GA, Tu AT (abril de 1977). "Protein sequencing by computer graphics". Biochim. Biofias. Acta. 491 (2): 605-8. doi:10.1016/0005-2795(77)90309-9. PMID 857910.
- ^ Jones, T.A. (agosto de 1978). "A Graphics Model Building and Refinement System for Macromolecules". Journal of Applied Crystallography. 11 (4): 268–272. doi:10.1107/S0021889878013308.
- ^ Jones, T. A. 1978b. El anillo [Manual de usuario]. Max-Planck-Institut fur Biochemie, 8033 Martinsried bei Muchen, Alemania.
- ^ Diamond, R. 1978. Bilder. Un programa de gráficos de computadora para bipolímeros y su aplicación a la interpretación de la estructura de los discos de proteínas del virus del tabaco en 2-A resolución. Proc. Unión Internacional de Bioquímica Pura y Aplicada: Simposio Internacional sobre Estructura, Conformación, Función y Evolución. Madras, India, (4 de enero), Pergamon Press.
- ^ Abagyan R, Lee WH, Raush E, et al. (febrero de 2006). "Describir datos de la genómica estructural al público: desde un vertedero de datos a una historia animada". Tendencias Biochem. Sci. 31 (2): 76–8. doi:10.1016/j.tibs.2005.12.006. PMID 16406633.
- ^ Raush E, Totrov M, Marsden BD, Abagyan R (2009). "Un nuevo método para publicar contenido tridimensional". PLOS ONE. 4 (10): e7394. Bibcode:2009PLoSO...4.7394R. doi:10.1371/journal.pone.0007394. PMC 2754609. PMID 19841676.
- ^ Wolfson, Haim; Duhovny, Dina; Tsherniak, Aviad. "Representación superficial molecular". www.cs.tau.ac.il. Retrieved 14 de junio 2022.
- ^ O'Donnell, TJ. "La ciencia y el arte de las superficies moleculares". www.cs.uic.edu. Retrieved 14 de junio 2022.
- ^ Smith, Thomas J. (27 de octubre de 2005). "Displaying and Analyzing Atomic Structures on the Macintosh". Danforth Plant Science Center. Archivado desde el original el 28 de marzo de 2002.
Enlaces externos
- Luminary Series Entrevista con Robert Langridge Entrevista de Russ Altman y diapositivas históricas.
- Historia de la visualización de macromoléculas biológicas por Eric Martz y Eric Francoeur.