Fago T7

El bacteriófago T7 (o fago T7) es un bacteriófago, un virus que infecta bacterias. Infecta a la mayoría de las cepas de Escherichia coli y depende de estos huéspedes para propagarse. El bacteriófago T7 tiene un ciclo de vida lítico, lo que significa que destruye la célula que infecta. También posee varias propiedades que lo convierten en un fago ideal para la experimentación: su purificación y concentración han producido valores consistentes en los análisis químicos; se puede volver no infeccioso mediante la exposición a la luz ultravioleta; y se puede utilizar en la visualización de fagos para clonar proteínas de unión al ARN.
Discovery
En un estudio de 1945 realizado por Demerec y Fano, se utilizó el término T7 para describir uno de los siete tipos de fagos (T1 a T7) que crecen líticamente en Escherichia coli; aunque los siete fagos se numeraron de forma arbitraria, más tarde se descubrió que los fagos con números impares, o fagos T-impares, compartían características morfológicas y bioquímicas que los diferenciaban de los fagos T-pares. Antes de que se lo denominara físicamente T7, el fago se utilizó en experimentos anteriores. El biofísico germano-estadounidense Max Delbrück trabajó con el mismo virus a fines de la década de 1930, llamándolo fago δ, y el microbiólogo franco-canadiense Félix d'Herelle probablemente estudió su pariente cercano en la década de 1920.
Hosts
T7 crece en cepas rugosas de Escherichia coli (es decir, aquellas que no tienen el polisacárido del antígeno O de longitud completa en su superficie) y en algunas otras bacterias entéricas, pero sus parientes cercanos también infectan cepas lisas e incluso encapsuladas.
Estructura de la virión
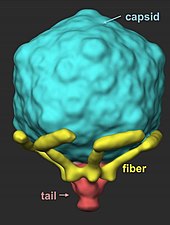

El virus tiene una simetría estructural compleja, con una cápside del fago que es icosaédrica (veinte caras) con un diámetro interno de 55 nm y una cola de 19 nm de diámetro y 28,5 nm de largo unida a la cápside. La expulsión de proteínas de la cápside tras la infección hace que el virus cambie de estructura cuando entra en la célula.
Genome
El genoma del fago T7 fue uno de los primeros genomas completamente secuenciados y se publicó en 1983. La cabeza de la partícula del fago contiene el genoma de dsADN de aproximadamente 40 kbp que codifica 55 proteínas. El genoma presenta numerosos genes superpuestos que se eliminaron parcialmente mediante la "refactorización" del genoma para producir T7.1.
Ciclo de vida
T7 tiene un ciclo de vida de 17 minutos a 37 ˚C, es decir, el tiempo que transcurre desde la infección hasta la lisis de la célula huésped cuando se liberan nuevos fagos. Debido al corto período de latencia, la mayoría de los estudios fisiológicos se realizan a 30 ˚C, donde las células infectadas se lisan después de 30 minutos. Sin embargo, se han aislado cepas de T7 de alta aptitud con un período de latencia de solo ~11 minutos a 37 ˚C que crecen en condiciones óptimas en medios ricos. Este fago adaptado puede experimentar una expansión efectiva de su población de más de 1013 en una hora de crecimiento.
Infección de bacterias anfitrionas




El fago T7 reconoce ciertos receptores en la superficie de las células de E. coli y se une a la superficie celular mediante las fibras de la cola viral. En algunas cepas de T7, las fibras de la cola se reemplazan por espigas que degradan los antígenos O o K en la superficie celular mediante la actividad enzimática.
El proceso de adsorción y penetración utiliza lisozimas para crear una abertura dentro de la capa de peptidoglicano de la pared celular bacteriana, lo que permite la transferencia del ADN viral a la bacteria. La cola corta y rechoncha del fago tipo T7 es demasiado corta para abarcar la envoltura celular y, para expulsar el genoma del fago dentro de la célula al inicio de la infección, las proteínas del virión primero deben hacer un canal desde la punta de la cola hasta el citoplasma celular. El fago también libera cinco proteínas necesarias para comenzar la replicación del genoma viral y escindir el genoma del huésped. El bacteriófago T7 ha evolucionado para anular varias de las defensas de la bacteria huésped, incluida la pared celular de peptidoglicano y el sistema CRISPR. Una vez que el fago T7 ha insertado el genoma viral, se detiene el proceso de replicación del ADN del genoma del huésped y comienza la replicación del genoma viral.
En condiciones óptimas, el fago T7 puede completar el proceso lítico en 25 minutos, lo que provoca la muerte de la célula huésped de E. coli. En el momento de la lisis, el virus puede producir más de 100 descendientes.
Componentes
La gp5 (codificada por el gen gp5) es la ADN polimerasa T7. La ADN polimerasa T7 utiliza la tiorredoxina endógena de E. coli, una proteína REDOX, como una abrazadera deslizante de ADN durante la replicación del ADN del fago (aunque la tiorredoxina normalmente tiene una función diferente). La abrazadera deslizante funciona para mantener la polimerasa sobre el ADN, lo que aumenta la tasa de síntesis.
Replicación y reparación de ADN
El fago T7 posee el replisoma de ADN más simple conocido, que consiste en una helicasa y una primasa que residen en una sola cadena polipeptídica que forma un hexámero en presencia de ADN y ATP o dTTP. La ADN polimerasa T7, asistida por la tiorredoxina de E. coli, realiza la síntesis de ADN de cadena líder y de cadena rezagada.
En el fago T7, las roturas de doble cadena de ADN probablemente se reparen mediante la inserción de un trozo de ADN donante en un hueco en el sitio de la rotura. Esta reparación de las roturas de doble cadena se ve facilitada por la proteína del gen 2.5, que promueve la hibridación de las cadenas complementarias homólogas de ADN.
Intermedios replicativos
El ADN intracelular replicante del fago T7, cuando se estira después de la lisis celular, suele ser más largo que el cromosoma maduro del fago (11 a 15 μM) y puede presentarse en forma de cadenas lineales altamente concatenadas de hasta 66 veces la longitud del cromosoma maduro del fago. El ADN replicante también se puede observar en forma de estructuras de anillo enrollado que parecen corresponder a configuraciones de ADN con múltiples bucles en las que los giros superhelicoidales, necesarios para la compactación del ADN, se aliviaron mediante cortes de las cadenas tras la lisis celular.
Aplicaciones en biología molecular
La secuencia promotora T7 se utiliza ampliamente en biología molecular debido a su altísima afinidad por la ARN polimerasa T7 y, por lo tanto, a su alto nivel de expresión.
T7 se ha utilizado como modelo en biología sintética. Chan et al. (2005) "refactorizaron" el genoma de T7, reemplazando aproximadamente 12 kbp de su genoma con ADN modificado. El ADN modificado se diseñó para que fuera más fácil trabajar con él de varias maneras: los elementos funcionales individuales se separaron mediante sitios de endonucleasas de restricción para una modificación simple, y los dominios codificantes de proteínas superpuestos se separaron y, cuando fue necesario, se modificaron mediante mutaciones silenciosas de un solo par de bases.
Referencias
- ^ Padilla-Sanchez, Victor (2021-07-10), Bacteriophage T7 Modelo Estructural en Resolución Atómica, doi:10.5281/zenodo.5133295, recuperado 2021-07-24
- ^ a b Studier, F. William (1969-11-01). "La genética y la fisiología del bacteriófago T7". Virología. 39 (3): 562–574. doi:10.1016/0042-6822(69)90104-4. ISSN 0042-6822. PMID 4902069.
- ^ a b c Teesalu, Tambet; Sugahara, Kazuki N.; Ruoslahti, Erkki (1 de enero de 2012). "Mapping of Vascular ZIP Codes by Phage Display". En Wittrup, K. Dane; Verdine, Gregory L. (eds.). Métodos en Enzimología. Academic Press. pp. 35–56. doi:10.1016/B978-0-12-396962-0.00002-1. PMID 22230564.
- ^ Demerec, M; Fano, U (15 de marzo de 1945). "Bacteriophage-Resistant Mutants in Escherichia coli". Genética. 30 (2): 119–136. doi:10.1093/genetics/30.2.119. PMC 1209279. PMID 17247150.
- ^ a b c d Häuser, Roman; Blasche, Sonja; Dokland, Terje; Haggård-Ljungquist, Elisabeth; von Brunn, Albrecht; Salas, Margarita; Casjens, Sherwood; Molineux, Ian; Uetz, Peter (2012). "Bacteriophage Protein-Protein Interactions". Avances en Investigación de Virus. 83: 219–298. doi:10.1016/B978-0-12-394438-2.00006-2. PMC 3461333. PMID 22748812.
- ^ Cammack, Richard; Atwood, Teresa; Campbell, Peter; Parish, Howard; Smith, Anthony; Vella, Frank; Stirling, John, eds. (2006). Oxford Dictionary of Biochemistry and Molecular Biology. Oxford University Press. doi:10.1093/acref/9780198529170.001.0001. ISBN 9780191727641.
- ^ D'Herelle, Félix (1926). El Bacteriophage y su comportamiento. Baltimore, MD: Williams & Wilkins. doi:10.5962/bhl.title.7308. LCCN 26009494. OCLC 2394374.
- ^ Molineux, Ian J. (2006). "Capítulo 20: El grupo T7". En Calendario, Richard Lane (ed.). Los Bacteriofagos (2a edición). Oxford: Oxford University Press. p. 277. ISBN 9780195148503.
- ^ "Teseptimavirus ~ ViralZone página". viralzone.expasy.org. Retrieved 2019-11-18.
- ^ Molineux, Ian J.; Panja, Debabrata (marzo de 2013). "Popping the cork: mechanisms of phage genome eyection". Reseñas de la naturaleza Microbiología. 11 (3): 194–204. doi:10.1038/nrmicro2988. ISSN 1740-1534. PMID 23385786. S2CID 205498472.
- ^ "Genoma de bacteriófago T7". 9 de septiembre de 2004. Retrieved 18 de mayo 2011.
- ^ Dunn, John J.; Studier, F. William; Gottesman, M. (junio de 1983). "Secuencia completa de nucleótido de ADN de bacteriófago T7 y de los elementos genéticos T7". Journal of Molecular Biology. 166 (4): 477-535. doi:10.1016/S0022-2836(83)80282-4. PMID 6864790.
- ^ "Uniprot: referencia proteome of bacteriophage T7".
- ^ Wright, Bradley W.; Molloy, Mark P.; Jaschke, Paul R. (2021-10-05). "Overlapping genes in natural and engineered genomes". Nature Reviews Genética. 23 (3): 154–168. doi:10.1038/s41576-021-00417-w. ISSN 1471-0064. PMC 8490965. PMID 34611352.
- ^ a b Chan, Leon Y; Kosuri, Sriram; Endy, Drew (enero de 2005). "Bateriafago factorial T7". Biología de sistemas moleculares. 1 (1). doi:10.1038/msb4100025. PMC 1681472. PMID 16729053.
- ^ Heineman, Richard H.; Bull, James J. (Julio 2007). "Testing Optimality With Experimental Evolution: Lysis Time in a Bacteriophage". Evolución. 61 (7): 1695–1709. doi:10.1111/j.1558-5646.2007.00132.x. PMC 1974807. PMID 17598749.
- ^ Chang, Chung-Yu; Kemp, Priscilla; Molineux, Ian J. (marzo de 2010). "Gp15 y gp16 cooperan en la transferencia de ADN de bacteriófago T7 a la célula infectada". Virología. 398 (2): 176–186. doi:10.1016/j.virol.2009.12.002. PMC 2825023. PMID 20036409.
- ^ a b c "New Details about Bacteriophage T7-Host Interactions". Archivado desde el original el 2011-08-17.
- ^ Kulczyk, A.W.; Richardson, C.C. (2016). "El Sistema de Replicación de Bacteriophage T7". Las Enzimas. 39: 89–136. doi:10.1016/bs.enz.2016.02.001. PMID 27241928.
- ^ Jeffery, Constance J. (1999-01-01). "Proteínas de iluminación". Tendencias en Ciencias Bioquímicas. 24 (1): 8–11. doi:10.1016/S0968-0004(98)01335-8. ISSN 0968-0004. PMID 10087914.
- ^ Lai, Ying‐Ta; Masker, Warren (abril de 2000). "Reparación de rupturas dobles por incorporación de una molécula de ADN homologoso". Microbiología molecular. 36 (2): 437-446. doi:10.1046/j.1365-2958.2000.01861.x. PMID 10792729.
- ^ Yu, Man; Masker, Warren (15 de marzo de 2001). "T7 Single Strand DNA Binding Protein pero no T7 Helicase es necesario para la reparación de doble fractura de ADN Strand". Journal of Bacteriology. 183 (6): 1862-1869. doi:10.1128/JB.183.6.1862-1869.2001. PMC 95080. PMID 11222583.
- ^ a b Bernstein, Carol; Bernstein, Harris (junio de 1974). "Anillos cubiertos de ADN liberados de células infectadas con Bacteriofagos T7 o T4 o de Escherichia coli no infectada". Journal of Virology. 13 (6): 1346–1355. doi:10.1128/JVI.13.6.1346-1355.1974. PMC 355455. PMID 4598784.
Enlaces externos
- T7+Phage en la Biblioteca Nacional de Medicina de EE.UU.
- ViralZone
- New Details about T7-host interactions. Microbe Magazine
- T7 referencia proteoma en Uniprot
![Schematic view of the phage T7 genome. Boxes are genes, numbers are gene numbers. Colors indicate functional groups as shown. White boxes are genes of unknown function or without annotation. Modified after [5]](https://upload.wikimedia.org/wikipedia/commons/thumb/d/db/T7_phage_genome.png/500px-T7_phage_genome.png)