Duplicación de genes
duplicación de genes (o duplicación cromosómica o amplificación de genes) es un mecanismo importante a través del cual se genera nuevo material genético durante la evolución molecular. Puede definirse como cualquier duplicación de una región del ADN que contiene un gen. Las duplicaciones de genes pueden surgir como producto de varios tipos de errores en la maquinaria de replicación y reparación del ADN, así como a través de captura fortuita por elementos genéticos egoístas. Las fuentes comunes de duplicaciones genéticas incluyen recombinación ectópica, evento de retrotransposición, aneuploidía, poliploidía y deslizamiento de replicación.
Mecanismos de duplicación
Recombinación ectópica
Las duplicaciones surgen de un evento denominado entrecruzamiento desigual que ocurre durante la meiosis entre cromosomas homólogos desalineados. La posibilidad de que esto suceda es función del grado de intercambio de elementos repetitivos entre dos cromosomas. Los productos de esta recombinación son una duplicación en el lugar del intercambio y una deleción recíproca. La recombinación ectópica suele estar mediada por la similitud de secuencia en los puntos de interrupción duplicados, que forman repeticiones directas. Los elementos genéticos repetitivos, como los elementos transponibles, ofrecen una fuente de ADN repetitivo que puede facilitar la recombinación y, a menudo, se encuentran en puntos de interrupción de la duplicación en plantas y mamíferos.
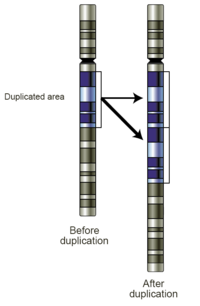
Deslizamiento de replicación
El deslizamiento de la replicación es un error en la replicación del ADN que puede producir duplicaciones de secuencias genéticas cortas. Durante la replicación, la ADN polimerasa comienza a copiar el ADN. En algún momento durante el proceso de replicación, la polimerasa se disocia del ADN y la replicación se detiene. Cuando la polimerasa se vuelve a unir a la cadena de ADN, alinea la cadena de replicación en una posición incorrecta y, de paso, copia la misma sección más de una vez. El deslizamiento de la replicación también suele verse facilitado por secuencias repetitivas, pero sólo requiere unas pocas bases de similitud.
Retrotransposición
Los retrotransposones, principalmente L1, pueden actuar ocasionalmente sobre el ARNm celular. Las transcripciones se transcriben de forma inversa a ADN y se insertan en un lugar aleatorio del genoma, creando retrogenes. La secuencia resultante generalmente carece de intrones y a menudo contiene polisecuencias que también están integradas en el genoma. Muchos retrogenes muestran cambios en la regulación genética en comparación con sus secuencias genéticas parentales, lo que a veces da como resultado funciones novedosas. Los retrogenes pueden moverse entre diferentes cromosomas para dar forma a la evolución cromosómica.
Aneuploidía
La aneuploidía ocurre cuando la falta de disyunción en un solo cromosoma da como resultado un número anormal de cromosomas. La aneuploidía suele ser perjudicial y en los mamíferos provoca regularmente abortos espontáneos (abortos espontáneos). Algunos individuos aneuploides son viables, por ejemplo la trisomía 21 en humanos, que conduce al síndrome de Down. La aneuploidía a menudo altera la dosis de genes de manera perjudicial para el organismo; por lo tanto, es poco probable que se propague entre las poblaciones.
Poliploidía
La poliploidía o duplicación del genoma completo es un producto de la no disyunción durante la meiosis que da como resultado copias adicionales del genoma completo. La poliploidía es común en plantas, pero también ha ocurrido en animales, con dos rondas de duplicación del genoma completo (evento 2R) en el linaje de vertebrados que conduce a los humanos. También ha ocurrido en las levaduras hemiascomicetas hace aproximadamente 100 millones de años.
Después de una duplicación completa del genoma, hay un período relativamente corto de inestabilidad del genoma, pérdida extensa de genes, niveles elevados de sustitución de nucleótidos y recableado de la red reguladora. Además, los efectos de la dosis genética desempeñan un papel importante. Por lo tanto, la mayoría de los duplicados se pierden en un corto período; sin embargo, una fracción considerable de los duplicados sobrevive. Curiosamente, los genes implicados en la regulación se conservan preferentemente. Además, la retención de genes reguladores, sobre todo los genes Hox, ha llevado a la innovación adaptativa.
Se ha observado una rápida evolución y divergencia funcional a nivel de la transcripción de genes duplicados, generalmente mediante mutaciones puntuales en motivos cortos de unión a factores de transcripción. Además, la rápida evolución de los motivos de fosforilación de proteínas, generalmente incrustados dentro de regiones intrínsecamente desordenadas que evolucionan rápidamente, es otro factor que contribuye a la supervivencia y la rápida adaptación/neofuncionalización de genes duplicados. Por tanto, parece existir un vínculo entre la regulación genética (al menos a nivel postraduccional) y la evolución del genoma.
La poliploidía también es una fuente bien conocida de especiación, ya que la descendencia, que tiene un número diferente de cromosomas en comparación con las especies originales, a menudo no puede cruzarse con organismos no poliploides. Se cree que las duplicaciones del genoma completo son menos perjudiciales que la aneuploidía, ya que la dosis relativa de genes individuales debería ser la misma.
Como evento evolutivo

Tasa de duplicación de genes
Las comparaciones de genomas demuestran que las duplicaciones de genes son comunes en la mayoría de las especies investigadas. Esto se indica mediante números de copias variables (variación del número de copias) en el genoma de los humanos o de las moscas de la fruta. Sin embargo, ha sido difícil medir el ritmo al que se producen dichas duplicaciones. Estudios recientes arrojaron una primera estimación directa de la tasa de duplicación de genes en todo el genoma en C. elegans, el primer eucariota multicelular del que se dispuso de estimaciones de este tipo. La tasa de duplicación de genes en C. elegans es del orden de 10−7 duplicaciones/gen/generación, es decir, en una población de 10 millones de gusanos, uno tendrá una duplicación genética por generación. Esta tasa es dos órdenes de magnitud mayor que la tasa espontánea de mutación puntual por sitio de nucleótido en esta especie. Estudios más antiguos (indirectos) informaron tasas de duplicación específicas de locus en bacterias, Drosophila y humanos que oscilaban entre 10−3 y 10−7/gen. /generación.
Neofuncionalización
Las duplicaciones de genes son una fuente esencial de novedad genética que puede conducir a la innovación evolutiva. La duplicación crea redundancia genética, donde la segunda copia del gen a menudo está libre de presión selectiva, es decir, sus mutaciones no tienen efectos nocivos para el organismo huésped. Si una copia de un gen experimenta una mutación que afecta su función original, la segunda copia puede servir como 'repuesto' y seguir funcionando correctamente. Así, los genes duplicados acumulan mutaciones más rápido que un gen funcional de una sola copia, a lo largo de generaciones de organismos, y es posible que una de las dos copias desarrolle una función nueva y diferente. Algunos ejemplos de tal neofuncionalización son la aparente mutación de un gen digestivo duplicado en una familia de peces de hielo en un gen anticongelante y la duplicación que conduce a un nuevo gen de veneno de serpiente y la síntesis de 1 beta-hidroxitestosterona en cerdos.
Se cree que la duplicación de genes desempeña un papel importante en la evolución; esta postura ha sido mantenida por miembros de la comunidad científica durante más de 100 años. Susumu Ohno fue uno de los desarrolladores más famosos de esta teoría en su libro clásico Evolución por duplicación de genes (1970). Ohno argumentó que la duplicación de genes es la fuerza evolutiva más importante desde la aparición del ancestro común universal. Los eventos importantes de duplicación del genoma pueden ser bastante comunes. Se cree que todo el genoma de la levadura se duplicó hace unos 100 millones de años. Las plantas son los duplicadores de genoma más prolíficos. Por ejemplo, el trigo es hexaploide (una especie de poliploide), lo que significa que tiene seis copias de su genoma.
Subfuncionalización
Otro posible destino de los genes duplicados es que ambas copias sean igualmente libres de acumular mutaciones degenerativas, siempre que cualquier defecto se complemente con la otra copia. Esto conduce a una "subfuncionalización" (un proceso de evolución neutral constructiva) o modelo DDC (duplicación-degeneración-complementación), en el que la funcionalidad del gen original se distribuye entre las dos copias. Ninguno de los genes se puede perder, ya que ahora ambos realizan importantes funciones no redundantes, pero en última instancia ninguno es capaz de lograr una nueva funcionalidad.
La subfuncionalización puede ocurrir a través de procesos neutrales en los que las mutaciones se acumulan sin efectos perjudiciales o beneficiosos. Sin embargo, en algunos casos la subfuncionalización puede ocurrir con claros beneficios adaptativos. Si un gen ancestral es pleiotrópico y realiza dos funciones, a menudo ninguna de estas dos funciones puede cambiarse sin afectar la otra función. De esta manera, dividir las funciones ancestrales en dos genes separados puede permitir la especialización adaptativa de subfunciones, proporcionando así un beneficio adaptativo.
Pérdida
A menudo, la variación genómica resultante conduce a trastornos neurológicos dependientes de la dosis genética, como el síndrome similar a Rett y la enfermedad de Pelizaeus-Merzbacher. Es probable que estas mutaciones perjudiciales desaparezcan de la población y no se conserven ni desarrollen funciones nuevas. Sin embargo, muchas duplicaciones, de hecho, no son perjudiciales ni beneficiosas, y estas secuencias neutrales pueden perderse o propagarse entre la población a través de fluctuaciones aleatorias a través de la deriva genética.
Did you mean:Identifying duplicates in sequenced genomes
Criterios y escaneos de genoma único
Los dos genes que existen después de un evento de duplicación genética se denominan parálogos y generalmente codifican proteínas con una función y/o estructura similar. Por el contrario, los genes ortólogos están presentes en diferentes especies y cada uno de ellos se deriva originalmente de la misma secuencia ancestral. (Ver Homología de secuencias en genética).
Es importante (pero a menudo difícil) diferenciar entre parálogos y ortólogos en la investigación biológica. Los experimentos sobre la función de los genes humanos a menudo pueden llevarse a cabo en otras especies si se puede encontrar un homólogo de un gen humano en el genoma de esa especie, pero sólo si el homólogo es ortólogo. Si son parálogos y resultan de un evento de duplicación genética, es probable que sus funciones sean demasiado diferentes. Una o más copias de genes duplicados que constituyen una familia de genes pueden verse afectadas por la inserción de elementos transponibles que provocan una variación significativa entre ellos en su secuencia y finalmente pueden convertirse en responsables de una evolución divergente. Esto también puede reducir las posibilidades y la tasa de conversión de genes entre los homólogos de duplicados de genes debido a una menor o ninguna similitud en sus secuencias.
Los parálogos se pueden identificar en genomas individuales mediante una comparación de secuencias de todos los modelos genéticos anotados entre sí. Dicha comparación se puede realizar en secuencias de aminoácidos traducidas (por ejemplo, BLASTp, tBLASTx) para identificar duplicaciones antiguas o en secuencias de nucleótidos de ADN (por ejemplo, BLASTn, megablast) para identificar duplicaciones más recientes. La mayoría de los estudios para identificar duplicaciones de genes requieren mejores coincidencias recíprocas o mejores coincidencias recíprocas difusas, donde cada parálogo debe ser la mejor coincidencia del otro en una comparación de secuencias.
La mayoría de las duplicaciones de genes existen como repeticiones de copias bajas (LCR), secuencias bastante repetitivas como elementos transponibles. Se encuentran principalmente en las regiones pericentronómica, subtelomérica e intersticial de un cromosoma. Muchos LCR, debido a su tamaño (>1Kb), similitud y orientación, son muy susceptibles a duplicaciones y eliminaciones.
Los microarrays genómicos detectan duplicaciones
Las tecnologías como los microarrays genómicos, también llamados hibridación genómica comparativa de matrices (CGH por sus siglas en inglés), se utilizan para detectar anomalías cromosómicas, como microduplicaciones, con un alto rendimiento a partir de muestras de ADN genómico. En particular, la tecnología de microarrays de ADN puede monitorear simultáneamente los niveles de expresión de miles de genes en muchos tratamientos o condiciones experimentales, lo que facilita enormemente los estudios evolutivos de la regulación genética después de la duplicación o especiación de genes.
Secuenciación de próxima generación
Las duplicaciones de genes también se pueden identificar mediante el uso de plataformas de secuenciación de próxima generación. El medio más sencillo para identificar duplicaciones en los datos de resecuenciación genómica es mediante el uso de lecturas de secuenciación de extremos emparejados. Las duplicaciones en tándem se indican mediante pares de lectura de secuenciación que se asignan en orientaciones anormales. Mediante una combinación de una mayor cobertura de secuencia y una orientación anormal del mapeo, es posible identificar duplicaciones en los datos de secuenciación genómica.
Nomenclatura
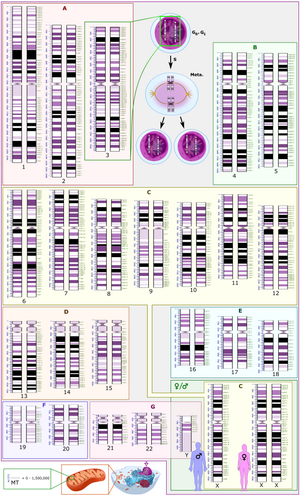
El Sistema Internacional de Nomenclatura Citogenómica Humana (ISCN) es un estándar internacional para la nomenclatura de los cromosomas humanos, que incluye nombres de bandas, símbolos y términos abreviados utilizados en la descripción de los cromosomas humanos y las anomalías cromosómicas. Las abreviaturas incluyen dup para duplicaciones de partes de un cromosoma. Por ejemplo, dup(17p12) causa la enfermedad de Charcot-Marie-Tooth tipo 1A.
Como amplificación
La duplicación de genes no constituye necesariamente un cambio duradero en el desarrollo de una especie. genoma. De hecho, estos cambios a menudo no duran más allá del organismo huésped inicial. Desde la perspectiva de la genética molecular, la amplificación genética es una de las muchas formas en que se puede sobreexpresar un gen. La amplificación genética puede ocurrir artificialmente, como ocurre con el uso de la técnica de reacción en cadena de la polimerasa para amplificar hebras cortas de ADN in vitro usando enzimas, o puede ocurrir naturalmente, como se describió anteriormente. Si se trata de una duplicación natural, aún puede tener lugar en una célula somática, en lugar de en una célula de la línea germinal (lo que sería necesario para un cambio evolutivo duradero).
Papel en el cáncer
Las duplicaciones de oncogenes son una causa común de muchos tipos de cáncer. En tales casos, la duplicación genética ocurre en una célula somática y afecta sólo al genoma de las propias células cancerosas, no a todo el organismo, y mucho menos a cualquier descendencia posterior. La reciente clasificación integral a nivel de paciente y la cuantificación de los eventos impulsores en cohortes TCGA revelaron que hay en promedio 12 eventos impulsores por tumor, de los cuales 1,5 son amplificaciones de oncogenes.
| Tipo de cáncer | Gene asociado amplificaciones | Prevalencia de amplificación en el tipo de cáncer (porcentaje) |
|---|---|---|
| Cáncer de mama | MYC | 20% |
| ERBB2 (HER2) | 20% | |
| CCND1 (Cyclin D1) | 15–20% | |
| FGFR1 | 12% | |
| FGFR2 | 12% | |
| Cáncer de cuello uterino | MYC | 25-50% |
| ERBB2 | 20% | |
| Cáncer colorrectal | HRAS | 30% |
| KRAS | 20% | |
| MYB | 15–20% | |
| Cáncer de esófago | MYC | 40% |
| CCND1 | 25% | |
| MDM2 | 13% | |
| Cáncer gástrico | CCNE (Cyclin E) | 15% |
| KRAS | 10% | |
| MET | 10% | |
| Glioblastoma | ERBB1 (EGFR) | 33–50% |
| CDK4 | 15% | |
| Cáncer de cabeza y cuello | CCND1 | 50% |
| ERBB1 | 10% | |
| MYC | 7-10% | |
| Cáncer hepatocelular | CCND1 | 13% |
| Neuroblastoma | MYCN | 20-25% |
| Cáncer de ovario | MYC | 20-30% |
| ERBB2 | 15-30% | |
| AKT2 | 12% | |
| Sarcoma | MDM2 | 10-30% |
| CDK4 | 10% | |
| Cáncer de pulmón de células pequeñas | MYC | 15–20% |
Las duplicaciones de todo el genoma también son frecuentes en los cánceres y se detectan en entre el 30% y el 36% de los tumores de los tipos de cáncer más comunes. Su papel exacto en la carcinogénesis no está claro, pero en algunos casos conducen a la pérdida de la segregación de la cromatina, lo que conduce a cambios en la conformación de la cromatina que a su vez conducen a modificaciones epigenéticas y transcripcionales oncogénicas.