ADN girasa
ADN girasa, o simplemente girasa, es una enzima dentro de la clase de las topoisomerasas y es una subclase de las topoisomerasas de tipo II que reduce la tensión topológica de una manera dependiente de ATP mientras El ADN bicatenario se desenrolla mediante la ARN polimerasa alargada o mediante la helicasa delante de la bifurcación de replicación en progreso. Es la única enzima conocida que contribuye activamente al superenrollamiento negativo del ADN, mientras que también es capaz de relajar los superenrollamientos positivos. Lo hace enrollando la plantilla para formar un cruce, luego cortando una de las dobles hélices y pasando la otra a través de ella antes de liberar la rotura, cambiando el número de enlace en dos en cada paso enzimático. Este proceso ocurre en bacterias, cuyo ADN circular único es cortado por la ADN girasa y luego los dos extremos se retuercen entre sí para formar superenrollamientos. La girasa también se encuentra en los plastidios eucariotas: se ha encontrado en el apicoplasto del parásito de la malaria Plasmodium falciparum y en los cloroplastos de varias plantas. La ADN girasa bacteriana es el objetivo de muchos antibióticos, incluidos el ácido nalidíxico, la novobiocina, la albicidina y la ciprofloxacina.
La capacidad única de la girasa para introducir superenrollamientos negativos en el ADN a expensas de la hidrólisis del ATP es lo que permite que el ADN bacteriano tenga superenrollamientos negativos libres. La capacidad de la girasa para relajar superenrollamientos positivos entra en juego durante la replicación del ADN y la transcripción procariótica. La naturaleza helicoidal del ADN hace que se acumulen superenrollamientos positivos delante de una enzima translocadora, en el caso de la replicación del ADN, una ADN polimerasa. La capacidad de la girasa (y la topoisomerasa IV) para relajar los superenrollamientos positivos permite que se libere la tensión superhélice delante de la polimerasa para que la replicación pueda continuar.
Estructura girasa
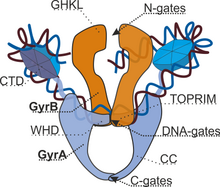
La ADN girasa es una enzima tetramérica que consta de 2 subunidades GyrA ("A") y 2 GyrB ("B"). Estructuralmente, el complejo está formado por 3 pares de "puertas", cuya apertura y cierre secuencial da como resultado la transferencia directa de un segmento de ADN y la introducción de 2 superenrollamientos negativos. Las puertas N están formadas por dominios ATPasa de las subunidades GyrB. La unión de 2 moléculas de ATP conduce a la dimerización y, por tanto, al cierre de las puertas. La hidrólisis, por el contrario, los abre. La escisión y reunión del ADN se realiza mediante un centro catalítico ubicado en las puertas del ADN construidas por todas las subunidades de girasa. Las puertas C están formadas por subunidades GyrA.
Modelo mecanoquímico de la actividad girasa

Un estudio de una sola molécula ha caracterizado la actividad de la girasa como una función de la tensión del ADN (fuerza aplicada) y del ATP, y ha propuesto un modelo mecanoquímico. Al unirse al ADN (el estado "ADN girasa"), existe una competencia entre la envoltura del ADN y la disociación, donde el aumento de la tensión del ADN aumenta la probabilidad de disociación. Según el ciclo catalítico propuesto, la unión de 2 moléculas de ATP provoca la dimerización de los dominios ATPasa de las subunidades GyrB y la captura de un segmento T de ADN (T- de transferencia) en una cavidad entre las subunidades GyrB. En el siguiente paso, la enzima escinde un segmento G de ADN (G- de puerta) rompiendo la doble hebra. Luego, el segmento T se transfiere a través de la rotura, lo que se acompaña de la hidrólisis de la primera molécula de ATP. La ADN girasa liga la rotura del segmento G y el segmento T finalmente abandona el complejo enzimático. La hidrólisis del segundo ATP devuelve el sistema al paso inicial de un ciclo. Como resultado de un ciclo catalítico se hidrolizan dos moléculas de ATP y se introducen dos superenrollamientos negativos en la plantilla de ADN. Se ha calculado que el número de vueltas superhélices introducidas en un ADN circular inicialmente relajado es aproximadamente igual al número de moléculas de ATP hidrolizadas por la girasa. Por lo tanto, se puede sugerir que la girasa hidroliza dos moléculas de ATP por ciclo de reacción, lo que lleva a la introducción de una diferencia de enlace de -2.
Especificidad de girasa
La girasa tiene una especificidad pronunciada por los sustratos de ADN. Se encontraron fuertes sitios de unión de girasa (SGS) en algunos fagos (grupo Mu del bacteriófago) y plásmidos (pSC101, pBR322). Recientemente, el mapeo de alto rendimiento de los sitios de ADN girasa en el genoma de Escherichia coli utilizando el enfoque Topo-Seq reveló un motivo de unión largo (≈130 pb) y degenerado que puede explicar la existencia de SGS. El motivo girasa refleja la envoltura del ADN alrededor del complejo enzimático y la flexibilidad del ADN. Contiene dos regiones periódicas en las que las islas ricas en GC se alternan con parches ricos en AT por un período cercano al período de la doble hélice del ADN (≈10,5 pb). Las dos regiones corresponden a la unión del ADN mediante los dominios C-terminales de las subunidades GyrA y se asemejan al motivo de unión del nucleosoma eucariota.
Inhibición por antibióticos
La girasa está presente en procariotas y algunos eucariotas, pero las enzimas no son completamente similares en estructura o secuencia, y tienen diferentes afinidades por diferentes moléculas. Esto hace que la girasa sea un buen objetivo para los antibióticos. Dos clases de antibióticos que inhiben la girasa son:
- Los aminocoumarins (incluyendo la novobiocina y la Coumermycina A1), que trabajan por la inhibición competitiva de la transducción de energía del yeso de ADN mediante la unión al sitio activo de ATPase en la subunidad GyrB.
- Los quinolones (incluyendo ácido nalidixico y ciprofloxacina) se conocen como venenos topoisomerasos. Al unirse a la enzima la atrapan en un paso transitorio del ciclo catalítico, evitando la reunión de un segmento G. Esto resulta en una acumulación de rupturas dobles, estancado de horquillas de replicación y muerte celular. Las bacterias resistentes a la quinolona suelen albergar topoisomeras mutadas que resisten la unión con la quinolona.
La subunidad A se inactiva selectivamente con antibióticos como los ácidos oxolínico y nalidíxico. La subunidad B se inactiva selectivamente con antibióticos como la cumermicina A1 y la novobiocina. La inhibición de cualquiera de las subunidades bloquea la actividad de supertorsión.
Fago T4
Los genes 39, 52 y 60 del fago T4 codifican proteínas que forman una ADN girasa que se emplea en la replicación del ADN del fago durante la infección de E. coli huésped bacteriano. La proteína del gen 52 del fago comparte homología con la subunidad gyrA de la girasa bacteriana y la proteína del gen 39 del fago comparte homología con la subunidad gyrB. Desde el anfitrión E. coli la ADN girasa puede compensar parcialmente la pérdida de los productos genéticos del fago, los mutantes defectuosos en cualquiera de los genes 39, 52 o 60 no suprimen completamente la replicación del ADN del fago, sino que retrasan su inicio. Los mutantes defectuosos en los genes 39, 52 o 60 muestran una mayor recombinación genética, así como una mayor sustitución de bases y mutaciones por deleción, lo que sugiere que la síntesis de ADN compensada por el huésped es menos precisa que la dirigida por fagos de tipo salvaje. Un mutante defectuoso en el gen 39 también muestra una mayor sensibilidad a la inactivación por irradiación ultravioleta durante la etapa de infección por fagos después del inicio de la replicación del ADN cuando están presentes múltiples copias del cromosoma del fago.