Filogenética
Em biologia, filogenética () é o estudo da história evolutiva e das relações entre ou dentro de grupos de organismos. Essas relações são determinadas por métodos de inferência filogenética que se concentram em características hereditárias observadas, como sequências de DNA, sequências de aminoácidos de proteínas ou morfologia. O resultado dessa análise é uma árvore filogenética - um diagrama contendo uma hipótese de relacionamentos que reflete a história evolutiva de um grupo de organismos.
As pontas de uma árvore filogenética podem ser táxons vivos ou fósseis e representam o "fim" ou o tempo presente em uma linhagem evolutiva. Um diagrama filogenético pode ser enraizado ou não enraizado. Um diagrama de árvore enraizada indica o ancestral comum hipotético da árvore. Um diagrama de árvore não enraizada (uma rede) não faz nenhuma suposição sobre a linha ancestral e não mostra a origem ou "raiz" dos táxons em questão ou a direção das transformações evolutivas inferidas.
Além de seu uso para inferir padrões filogenéticos entre táxons, as análises filogenéticas são frequentemente empregadas para representar relações entre genes ou organismos individuais. Tais usos tornaram-se centrais para a compreensão da biodiversidade, evolução, ecologia e genomas.
A filogenética é o componente da sistemática que usa as semelhanças e diferenças das características das espécies para interpretar suas relações evolutivas e origens. A filogenética se concentra em saber se as características de uma espécie reforçam uma inferência filogenética de que ela divergiu do ancestral comum mais recente de um grupo taxonômico.
No campo da pesquisa do câncer, a filogenética pode ser usada para estudar a evolução clonal de tumores e a cronologia molecular, prevendo e mostrando como as populações de células variam ao longo da progressão da doença e durante o tratamento, usando técnicas de sequenciamento do genoma completo. Os processos evolutivos por trás da progressão do câncer são bastante diferentes daqueles nas espécies e são importantes para a inferência filogenética; essas diferenças se manifestam em pelo menos quatro áreas: os tipos de aberrações que ocorrem, as taxas de mutação, a intensidade e a alta heterogeneidade - variabilidade - dos subclones de células tumorais.
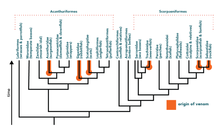
A filogenética também pode ajudar na concepção e descoberta de medicamentos. A filogenética permite aos cientistas organizar as espécies e pode mostrar quais espécies provavelmente herdaram características particulares que são úteis do ponto de vista médico, como a produção de compostos biologicamente ativos - aqueles que têm efeitos no corpo humano. Por exemplo, na descoberta de drogas, os animais produtores de veneno são particularmente úteis. Os venenos desses animais produzem várias drogas importantes, como os inibidores da ECA e o Prialt (Ziconotide). Para encontrar novos venenos, os cientistas recorrem à filogenia para rastrear espécies intimamente relacionadas que possam ter as mesmas características úteis. A árvore filogenética mostra quais espécies de peixes têm uma origem de veneno e peixes relacionados que podem conter a característica. Usando essa abordagem no estudo de peixes venenosos, os biólogos são capazes de identificar as espécies de peixes que podem ser venenosas. Os biólogos usaram essa abordagem em muitas espécies, como cobras e lagartos. Na ciência forense, as ferramentas filogenéticas são úteis para avaliar evidências de DNA para processos judiciais. A árvore filogenética simples dos vírus A-E mostra as relações entre os vírus, por exemplo, todos os vírus são descendentes do vírus A.
A análise forense do HIV usa análise filogenética para rastrear as diferenças nos genes do HIV e determinar a relação de duas amostras. A análise filogenética tem sido usada em julgamentos criminais para exonerar ou prender indivíduos. A análise forense do HIV tem suas limitações, ou seja, não pode ser a única prova de transmissão entre indivíduos e a análise filogenética que mostra o parentesco da transmissão não indica a direção da transmissão.
Taxonomia e classificação
Taxonomia é a identificação, nomeação e classificação de organismos. Em comparação com a sistematização, a classificação enfatiza se uma espécie possui características de um grupo taxonômico. O sistema de classificação Linnaean desenvolvido em 1700 por Carolus Linnaeus é a base para métodos de classificação modernos. A classificação de Lineu depende do fenótipo de um organismo ou das características físicas para agrupar e organizar as espécies. Com o surgimento da bioquímica, as classificações de organismos agora são geralmente baseadas em dados filogenéticos, e muitos sistematas afirmam que apenas os táxons monofiléticos devem ser reconhecidos como grupos nomeados. O grau em que a classificação depende da história evolutiva inferida difere dependendo da escola de taxonomia: a fenética ignora completamente a especulação filogenética, tentando representar a semelhança entre os organismos; a cladística (sistemática filogenética) tenta refletir a filogenia em suas classificações reconhecendo apenas grupos baseados em caracteres derivados compartilhados (sinapomorfias); a taxonomia evolutiva tenta levar em conta tanto o padrão de ramificação quanto o "grau de diferença" para encontrar um meio-termo entre eles.
Inferência de uma árvore filogenética
Métodos usuais de inferência filogenética envolvem abordagens computacionais que implementam os critérios de otimização e métodos de parcimônia, máxima verossimilhança (ML) e inferência bayesiana baseada em MCMC. Tudo isso depende de um modelo matemático implícito ou explícito que descreve a evolução dos caracteres observados.
A fenética, popular em meados do século 20, mas agora amplamente obsoleta, usava métodos baseados em matrizes de distância para construir árvores com base na semelhança geral na morfologia ou em características observáveis semelhantes (ou seja, no fenótipo ou na semelhança geral do DNA, não na sequência de DNA), que muitas vezes se supunha aproximar as relações filogenéticas.
Antes de 1950, as inferências filogenéticas eram geralmente apresentadas como cenários narrativos. Esses métodos costumam ser ambíguos e carecem de critérios explícitos para avaliar hipóteses alternativas.
Impactos da amostragem de táxons
Na análise filogenética, a amostragem de táxons seleciona um pequeno grupo de táxons para representar a história evolutiva de sua população mais ampla. Esse processo também é conhecido como amostragem estratificada ou amostragem baseada em clados. A prática ocorre com recursos limitados para comparar e analisar todas as espécies dentro de uma população-alvo. Com base no grupo representativo selecionado, a construção e a precisão das árvores filogenéticas variam, o que afeta as inferências filogenéticas derivadas.
Conjuntos de dados indisponíveis, como DNA incompleto de um organismo e sequências de aminoácidos de proteínas em bancos de dados genômicos, restringem diretamente a amostragem taxonômica. Consequentemente, uma fonte significativa de erro na análise filogenética ocorre devido a amostras inadequadas de táxons. A precisão pode ser melhorada aumentando o número de amostras genéticas dentro de seu grupo monofilético. Por outro lado, aumentar a amostragem de grupos estranhos à população estratificada alvo pode diminuir a precisão. A atração de galhos longos é uma teoria atribuída a essa ocorrência, onde galhos não relacionados são incorretamente classificados juntos, insinuando uma história evolutiva compartilhada.

Há debates se aumentar o número de taxa amostrados melhora a precisão filogenética mais do que aumentar o número de genes amostrados por táxon. As diferenças na amostragem de cada método afetam o número de sítios de nucleotídeos utilizados em um alinhamento de sequência, o que pode contribuir para divergências. Por exemplo, as árvores filogenéticas construídas utilizando um número mais significativo de nucleotídeos totais são geralmente mais precisas, conforme sustentado por árvores filogenéticas. replicabilidade bootstrapping de amostragem aleatória.
O gráfico apresentado em Amostragem de táxons, bioinformática e filogenômica compara a exatidão das árvores filogenéticas geradas usando menos táxons e mais sítios por táxon no eixo x com mais táxons e menos sítios por táxon no eixo y. Com menos táxons, mais genes são amostrados no grupo taxonômico; em comparação, com mais táxons adicionados ao grupo de amostragem taxonômica, menos genes são amostrados. Cada método tem o mesmo número total de locais de nucleotídeos amostrados. Além disso, a linha pontilhada representa uma precisão de 1:1 entre os dois métodos de amostragem. Como visto no gráfico, a maioria dos pontos plotados está localizada abaixo da linha pontilhada, o que indica uma maior precisão ao amostrar menos táxons com mais sítios por táxon. A pesquisa realizada utiliza quatro diferentes modelos de construção de árvores filogenéticas para verificar a teoria; junção de vizinhos (NJ), evolução mínima (ME), parcimônia máxima não ponderada (MP) e verossimilhança máxima (ML). Na maioria dos modelos, amostrar menos táxons com mais sítios por táxon demonstrou maior precisão.
Geralmente, com o alinhamento de um número relativamente igual de locais totais de nucleotídeos, a amostragem de mais genes por táxon tem maior replicabilidade de inicialização do que a amostragem de mais táxons. No entanto, conjuntos de dados desequilibrados dentro de bancos de dados genômicos tornam cada vez mais difícil aumentar a comparação de genes por táxon em organismos raramente amostrados.
História
Visão geral
O termo "filogenia" deriva do alemão Phylogenie, introduzido por Haeckel em 1866, e a abordagem darwiniana para a classificação ficou conhecida como & #34;filético" abordagem. Pode ser rastreada até Aristóteles, que escreveu em seus Análise Posterior: “Podemos assumir a superioridade ceteris paribus [outras coisas sendo iguais] da demonstração que deriva de menos postulados ou hipóteses”.
Teoria da recapitulação de Ernst Haeckel
O conceito moderno de filogenética evoluiu principalmente como uma refutação de uma teoria anteriormente amplamente aceita. Durante o final do século 19, a teoria da recapitulação de Ernst Haeckel, ou "lei biogenética fundamental", foi amplamente aceita. Muitas vezes foi expresso como "ontogenia recapitula a filogenia", ou seja, o desenvolvimento de um único organismo durante sua vida, de germe a adulto, espelha sucessivamente os estágios adultos de sucessivos ancestrais da espécie à qual pertence. Mas essa teoria há muito foi rejeitada. Em vez disso, a ontogenia evolui - a história filogenética de uma espécie não pode ser lida diretamente de sua ontogenia, como Haeckel pensou que seria possível, mas os caracteres da ontogenia podem ser (e têm sido) usados como dados para análises filogenéticas; quanto mais próximas duas espécies são, mais apomorfias seus embriões compartilham.
Linha do tempo dos pontos-chave
- Século XIV, lex parsimoniae (princípio parsimony), Guilherme de Ockam, filósofo inglês, teólogo e frade franciscano, mas a ideia realmente remonta a Aristóteles, como um conceito precursor. Ele introduziu o conceito de navalha de Occam, que é o princípio de solução de problemas que recomenda procurar explicações construídas com o menor conjunto possível de elementos. Embora ele não tenha usado essas palavras exatas, o princípio pode ser resumido como “As entidades não devem ser multiplicadas além da necessidade”. O princípio defende que, quando apresentado com hipóteses concorrentes sobre a mesma previsão, deve-se preferir aquele que requer menos suposições.
- 1763, probabilidade bayesiana, Rev. Thomas Bayes, um conceito precursor. A probabilidade bayesiana começou um ressurgimento na década de 1950, permitindo que os cientistas no campo da computação emparelhassem estatísticas tradicionais da Bayesian com outras técnicas mais modernas. Agora é usado como um termo cobertor para várias interpretações relacionadas da probabilidade como uma quantidade de confiança epistêmica.
- O século XVIII, Pierre Simon (Marquis de Laplace), talvez primeiro a usar ML (possibilidade máxima), conceito precursor. Seu trabalho deu lugar à distribuição Laplace, que pode ser diretamente ligado a desvios menos absolutos.
- 1809, teoria evolutiva, Filosofia Zoologique, Jean-Baptiste de Lamarck, conceito precursor, prenunciado no século XVII e século XVIII por Voltaire, Descartes e Leibniz, com Leibniz mesmo propondo mudanças evolutivas para explicar lacunas observadas sugerindo que muitas espécies haviam se tornado extintas, outras transformadas, e diferentes espécies que compartilham traços comuns podem ter sido uma única raça, também prenunciada por alguns filósofos gregos antigos como Anaditom
- 1837, os cadernos de Darwin mostram uma árvore evolutiva
- 1840, o geólogo americano Edward Hitchcock publicou o que é considerado o primeiro paleontológico “Tree of Life”. Muitas críticas, modificações e explicações seguiriam.
- 1843, distinção entre homologia e analogia (a última agora referida como homoplasia), Richard Owen, conceito precursor. Homologia é o termo usado para caracterizar a semelhança de características que podem ser explicadas parsimoniamente pela ancestralidade comum. Homoplasy é o termo usado para descrever um recurso que foi ganho ou perdido independentemente em linhagens separadas ao longo da evolução.
- 1858, Paleontologist Heinrich Georg Bronn (1800-1862) publicou uma árvore hipotética para ilustrar o "arrival" paleontológico de novas espécies semelhantes após a extinção de uma espécie mais antiga. Bronn não propôs um mecanismo responsável por tais fenômenos, conceito precursor.
- 1858, elaboração da teoria evolutiva, Darwin e Wallace, também em Origin of Species por Darwin no ano seguinte, conceito precursor
- 1866, Ernst Haeckel, publica pela primeira vez sua árvore evolutiva baseada em filogenia, conceito precursor. Haeckel apresenta a teoria de recapitulação agora reprovada.
- 1893, Lei de Irreversibilidade do Estado de Caráter, conceito precursor. A Lei de Irreversibilidade de Dollo afirma que “um organismo nunca volta exatamente ao seu estado anterior devido à natureza indestrutível do passado, ele sempre mantém algum traço das etapas de transição através das quais passou. ”
- 1912, ML (possibilidade máxima recomendada, analisada e popularizada por Ronald Fisher, conceito precursor. Fisher é um dos principais contribuintes para o início do século XX avivamento do darwinismo, e foi chamado de “grande dos sucessores de Darwin” por suas contribuições para a revisão da teoria da evolução e seu uso da matemática para combinar a genética mendeliana e seleção natural no século XX "síntese moderna".
- 1921, Tillyard usa o termo "filogenético" e distingue entre personagens arcaicos e especializados em seu sistema de classificação
- 1940, termo "clade" cunhado por Lucien Cuénot
- 1949, Jackknife resampling, Maurice Quenouille (prenuado em '46 por Mahalanobis e estendido em '58 por Tukey), conceito precursor
- 1950, a formalização clássica de Willi Hennig. Hennig é considerado o fundador da sistemática filogenética, e publicou suas primeiras obras em alemão deste ano. Ele também afirmou uma versão do princípio parsimony, afirmando que a presença de personagens amorfos em diferentes espécies "é sempre razão para suspeitar de parentesco, e que sua origem por convergência não deve ser presumida a priori". Isto foi considerado uma visão fundamental da inferência filogenética.
- 1952, método de divergência de plano de terra de William Wagner
- 1953, "cladogenesis" cunhado
- 1960, "cladistic" cunhado por Cain e Harrison
- 1963, primeira tentativa de usar ML (possibilidade máxima) para filogenética, Edwards e Cavalli-Sforza
- 1965
- Camin-Sokal parsimony, primeiro critério de parsimony (optimization) e primeiro programa de computador/algorithm para análise cladistic tanto por Camin e Sokal
- método de compatibilidade de caracteres, também chamado de análise clique, introduzido independentemente por Camin e Sokal (loc. cit.) e E. O. Wilson
- 1966
- Inglês translation of Hennig
- "cladistics" e "cladogram" cunhados (Webster's, loc. cit.)
- 1969
- ponderação dinâmica e sucessiva, James Farris
- Wagner parsimony, Kluge e Farris
- CI (índice de consistência), Kluge e Farris
- introdução de compatibilidade em pares para análise de cliques, Le Quesne
- 1970, Wagner parsimony generalizado por Farris
- 1971
- primeira aplicação bem sucedida de ML (possibilidade máxima) para filogenética (para sequências de proteínas), Neyman
- Fitch parsimony, Walter M. Fitch. Estes deram lugar às ideias mais básicas do parsimony máximo. Fitch é conhecido por seu trabalho em reconstruir árvores filogenéticas de sequências de proteínas e DNA. Sua definição de sequências ortodoxas foi referenciada em muitas publicações de pesquisa.
- NNI (intercâmbio mais próximo), primeira estratégia de busca de quebra de ramos, desenvolvida independentemente por Robinson e Moore et al.
- ME (volução mínima), Kidd e Sgaramella-Zonta (não é claro se este é o método de distância emparelhado ou relacionado com ML como Edwards e Cavalli-Sforza chamam ML " Evolução mínima")
- 1972, Adams consenso, Adams
- 1976, prefix system for ranks, Farris
- 1977, Dollo parsimony, Farris
- 1979
- Nelson consenso, Nelson
- MAST (máximo acordo subárvore)((GAS) maior acordo subárvore), um método de consenso, Gordon
- bootstrap, Bradley Efron, conceito precursor
- 1980, PHYLIP, primeiro pacote de software para análise filogenética, Joseph Felsenstein. Um pacote filogenético computacional gratuito de programas para inferir árvores evolucionárias (filogenias). Uma árvore de exemplo criada por PHILYP, chamada de "drawgram", gera árvores enraizadas. Esta imagem mostrada na figura abaixo mostra a evolução das árvores filogenéticas ao longo do tempo.
- 1981
- consenso da maioria, Margush e MacMorris
- consenso rigoroso, Sokal e Rohlfprimeiro algoritmo de ML computacionalmente eficiente (máximo probabilidade). Felsenstein criou o método Felsenstein Maximum Likelihood, usado para a inferência da filogenia que avalia uma hipótese sobre a história evolucionária em termos da probabilidade de que o modelo proposto e a história hipotética daria origem ao conjunto de dados observado.
- 1982
- PHYSIS, Mikevich e Farris
- ramo e amarrado, Hendy e Penny
- 1985
- primeira análise cladística de eucariotes com base em evidências fenotípicas e genótípicas combinadas Diana Lipscomb
- primeira edição de Cladistics
- primeira aplicação filogenética de bootstrap, Felsenstein
- primeira aplicação filogenética de jackknife, Scott Lanyon
- 1986, MacClade, Maddison e Maddison
- 1987, método vizinho Saitou e Nei
- 1988, Hennig86 (versão 1.5), Farris
- Suporte de Bremer (índice de decadência), Bremer
- 1989
- RI (índice de retenção), RCI (índice de consistência reduzido), Farris
- HER (taxa de excesso de homoplasia), Archie
- 1990
- Componentes combinable (semi-strict) consenso, Bremer
- SPR (subtree pruning e reversão), TBR (bisecção de árvores e reconexão), Swofford e Olsen
- 1991
- DDI (índice de determinação de dados), Goloboff
- primeira análise cladística de eucariotes baseada apenas em evidências fenotípicas, Lipscomb
- 1993, peso implícito Goloboff
- 1994, redução do consenso: RCC (reduzido consenso cladístico) para árvores enraizadas, Wilkinson
- 1995, redução do consenso RPC (reduzido consenso de partição) para árvores não desraizadas, Wilkinson
- 1996, primeiros métodos de trabalho para BI (InferênciaBayesiana) desenvolvidos independentemente por Li, Mau, e Rannala e Yang e todos usando MCMC (Markov chain-Monte Carlo)
- 1998 TNT (Análise de Três Usando Nova Tecnologia), Goloboff, Farris e Nixon
- 1999 Winclada, Nixon
- 2003, reformulação simétrica, Goloboff
- 2004,2005, similaridade métrica (usando uma aproximação à complexidade de Kolmogorov) ou NCD (distância de compressão normalizada), Li et al., Cilibrasi e Vitanyi.
Fora da biologia
As ferramentas e representações filogenéticas (árvores e redes) também podem ser aplicadas à filologia, ao estudo da evolução das línguas orais e dos textos e manuscritos escritos, como no campo da linguística comparativa quantitativa.
A filogenética computacional pode ser usada para investigar uma língua como um sistema evolutivo. A evolução da linguagem humana corresponde de perto à evolução biológica humana, o que permite a aplicação de métodos filogenéticos. O conceito de uma "árvore" serve como uma maneira eficiente de representar relacionamentos entre idiomas e divisões de idiomas. Também serve como uma forma de testar hipóteses sobre as conexões e idades das famílias linguísticas. Por exemplo, relacionamentos entre idiomas podem ser mostrados usando cognatos como caracteres. A árvore filogenética das línguas indo-européias mostra as relações entre várias línguas em uma linha do tempo, bem como a semelhança entre as palavras e a ordem das palavras.
Existem três tipos de críticas ao uso da filogenética na filologia, a primeira argumentando que línguas e espécies são entidades diferentes, portanto não se pode usar os mesmos métodos para estudar ambas. A segunda é como os métodos filogenéticos estão sendo aplicados aos dados linguísticos. E o terceiro, discute os tipos de dados que estão sendo usados para construir as árvores.
Métodos filogenéticos bayesianos, que são sensíveis a quão arborescentes são os dados, permitem a reconstrução de relações entre idiomas, local e globalmente. As duas principais razões para o uso da filogenética bayesiana são que (1) diversos cenários podem ser incluídos nos cálculos e (2) a saída é uma amostra de árvores e não uma única árvore com reivindicação verdadeira.
O mesmo processo pode ser aplicado a textos e manuscritos. Na Paleografia, o estudo de escritos e manuscritos históricos, os textos eram replicados por escribas que copiavam de sua fonte e alterações - isto é, "mutações" - ocorriam quando o escriba não copiava precisamente a fonte.
Triagem filogenética no papel da biodiversidade
As telas filogenéticas envolvem o exame farmacológico de grupos de organismos intimamente relacionados. Avanços na análise cladística por meio de programas computacionais rápidos e técnicas moleculares melhoraram a precisão da determinação filogenética, permitindo a identificação de espécies com potencial farmacológico. As telas filogenéticas foram usadas de maneira rudimentar no passado, como o estudo da família Apocynaceae de plantas conhecidas por suas espécies produtoras de alcaloides, como Catharanthus, que produz vincristina, um medicamento antileucemia. No entanto, as técnicas modernas agora permitem que os pesquisadores estudem parentes próximos de uma espécie para descobrir (1) maior abundância de compostos bioativos importantes (por exemplo, espécies de Taxus para taxol) ou (2) variantes naturais de produtos farmacêuticos conhecidos (por exemplo, espécies de Catharanthus para diferentes formas de vincristina ou vinblastina.
Observando a Fig 6. contém a tela filogenética da biodiversidade dentro da família dos fungos. Como visto dentro do círculo, existem subárvores presentes que foram feitas por meio de análise filogenética. Essas relações ajudam a entender a história evolutiva de vários grupos de organismos, identificando relações entre diferentes espécies e prevendo futuras mudanças evolutivas. Se fôssemos pegar informações sobre biodiversidade a partir do conhecimento existente, poderia haver relações entre espécies ou subgrupos que não conhecíamos. Mas com sistemas de imagens emergentes e novas técnicas de análise, mais relações genéticas podem ser encontradas em campos biodiversos. A imagem abaixo pode ajudar nos esforços de conservação, pois há espécies raras de fungos envolvidas, que podem ser benéficas para os ecossistemas ao redor.
Árvore filogenética molda insights sobre padrões de transmissão de doenças
Os dados da sequência do genoma completo de patógenos obtidos de surtos ou epidemias de doenças infecciosas podem fornecer informações importantes sobre a dinâmica de transmissão e informar estratégias de saúde pública. Estudos anteriores contaram com a integração de dados genômicos e epidemiológicos para reconstruir eventos de transmissão. No entanto, pesquisas recentes exploraram a possibilidade de deduzir padrões de transmissão apenas a partir de dados genômicos usando a filogenia, que envolve a análise das propriedades das filogenias do patógeno. A filodinâmica usa modelos teóricos para comparar comprimentos de ramificação previstos com comprimentos de ramificação reais em filogenias para inferir padrões de transmissão. Além disso, a teoria coalescente, que descreve distribuições de probabilidade em árvores com base no tamanho da população, foi adaptada para fins epidemiológicos. Outra fonte potencial de informação dentro das filogenias que tem sido explorada é a "forma da árvore". Essas abordagens são computacionalmente intensivas, mas têm o potencial de fornecer informações valiosas sobre a dinâmica de transmissão de patógenos.
A estrutura da rede de contato do hospedeiro tem um impacto profundo na dinâmica de surtos ou epidemias, e as estratégias de gerenciamento de surtos dependem do tipo de padrões de transmissão que conduzem ao surto. Pode-se esperar que os genomas de patógenos que se espalham por diferentes estruturas de rede de contato, como cadeias, redes homogêneas ou redes com super espalhadores, acumulem mutações em padrões distintos, resultando em diferenças perceptíveis na forma das árvores filogenéticas, conforme ilustrado na Fig. 1. Foi realizada a análise das características estruturais das árvores filogenéticas geradas a partir da evolução simulada do genoma bacteriano em vários tipos de redes de contato. Propriedades topológicas simples de árvores filogenéticas que, quando combinadas, podem ser usadas para classificar árvores em dinâmicas em cadeia, homogêneas ou super espalhadas, revelando a dinâmica de transmissão. Essas propriedades formam a base de um classificador computacional usado para classificar surtos do mundo real. Notavelmente, as previsões computacionais da dinâmica geral de transmissão para cada surto se alinham com a epidemiologia conhecida
Diferentes redes de transmissão resultam em formas de árvore quantitativamente diferentes Para determinar se as formas de árvore capturaram informações sobre os padrões de transmissão de doenças subjacentes em um surto, simulamos a evolução de um genoma bacteriano em três tipos de rede de contato de surto - homogênea, super espalhada e cadeia - e resumiu as filogenias resultantes com cinco métricas que descrevem a forma da árvore. As Figuras 2 e 33 ilustram as distribuições dessas métricas nos três tipos de surtos, revelando diferenças claras na topologia da árvore, dependendo da rede de contato do host subjacente. Redes superespalhadoras deram origem a filogenias com maior desequilíbrio de Colless, padrões de escada mais longos, menor Δw e árvores mais profundas do que redes de transmissão com distribuição homogênea de contatos. As árvores derivadas de redes semelhantes a cadeias eram menos variáveis, mais profundas, mais desequilibradas e mais estreitas do que as outras árvores. Outras métricas de resumo topológico consideradas não resolveram os três tipos de surto tão completamente (Informações Suplementares). Os gráficos de dispersão podem ser usados para análise de transmissão de patógenos para visualizar a relação entre duas variáveis, como o número de indivíduos infectados e o tempo desde a infecção. Por exemplo, um gráfico de dispersão pode ser usado para examinar a relação entre o número de casos de um patógeno e a quantidade de tempo desde que o primeiro caso foi relatado. Isso pode ajudar a identificar tendências e padrões nos dados, como se a disseminação do patógeno está aumentando ou diminuindo com o tempo. Os gráficos de dispersão também podem ser usados para identificar quaisquer outliers ou clusters de pontos de dados, o que pode fornecer informações sobre possíveis rotas de transmissão ou eventos de superespalhamento. No geral, os gráficos de dispersão podem ser uma ferramenta útil na análise de transmissão de patógenos para identificar padrões e tendências nos dados e para informar intervenções de saúde pública e medidas de controle.
As imagens do box plot à direita exibem os dados de transformação do patógeno. Box plots são frequentemente usados em análises estatísticas para comparar diferentes grupos ou para visualizar mudanças em um único grupo ao longo do tempo. Eles são particularmente úteis ao lidar com grandes conjuntos de dados ou ao comparar vários grupos, pois podem destacar rapidamente diferenças ou semelhanças nos dados. Box plots, também conhecidos como box-and-whisker plots, são úteis na análise estatística para fornecer um resumo da distribuição de um conjunto de dados. Eles exibem o intervalo, a mediana, os quartis e possíveis outliers dos dados de maneira visual. Box plots são comumente usados para comparar diferentes grupos ou para analisar mudanças em um único grupo ao longo do tempo. Eles são especialmente úteis ao trabalhar com grandes conjuntos de dados ou ao comparar vários grupos, pois podem identificar facilmente quaisquer diferenças ou semelhanças nos dados. Isso torna os gráficos de caixa uma ferramenta valiosa para analisar dados de transmissão de patógenos, pois podem ajudar a identificar características importantes na distribuição dos dados.